2. \(k\)-NN#
Introducción
El algoritmo vecino más cercano es considerado uno de los más simples dentro del aprendizaje automático. Su enfoque consiste en memorizar el conjunto de entrenamiento y luego predecir la etiqueta del vecino más cercano en dicho conjunto. Este método se basa en la idea de que las características utilizadas para describir los puntos en el dominio son relevantes para determinar sus etiquetas, de manera que es probable que puntos cercanos tengan la misma etiqueta. Incluso en situaciones donde el conjunto de entrenamiento es muy grande, es posible encontrar un vecino más cercano, como por ejemplo cuando el conjunto de entrenamiento abarca toda la Web y las distancias se basan en enlaces.
A diferencia de otros paradigmas algorítmicos que requieren hipótesis predefinidas, el método del vecino más cercano calcula una etiqueta para cualquier punto de prueba sin buscar un predictor dentro de una clase de funciones predefinida. En este capítulo, se describen los métodos del vecino más cercano tanto para problemas de clasificación como de regresión, se analiza su rendimiento en clasificación binaria y se discute la eficacia de su aplicación.
2.1. Análisis#
Definition 2.1 (\(k\)-NN (Clasificación))
Sea \(\mathcal{X}\) nuestro dominio de instancia (conjunto de objetos que se desea etiquetar), dotado con una métrica \(\rho\). Es decir, \(\rho:\mathcal{X}\times\mathcal{X}\longrightarrow\mathbb{R}\) es una función que retorna la distancia entre cualquier par de elementos de \(\mathcal{X}\). Por ejemplo, si \(\mathcal{X}=\mathbb{R}^{d}\), entonces \(\rho\) puede ser la distancia Euclidiana,
Sea \(S=(\boldsymbol{x}_{1}, y_{1}),\dots,(\boldsymbol{x}_{m}, y_{m})\) una secuencia de ejemplos de entrenamiento y \(\mathcal{Y}\), el conjunto de etiquetas, usualmente: \(\{0, 1\},~\{-1, +1\}\) o \(\mathbb{R}\). Para cada \(\boldsymbol{x}\in\mathcal{X}\), sea \(\pi_{1}(\boldsymbol{x}),\dots,\pi_{m}(\boldsymbol{x})\) una reordenación de \(\{1,\dots,m\}\) en función de su distancia a \(\boldsymbol{x}\), \(\rho(\boldsymbol{x}, \boldsymbol{x}_{i})\). Esto es, para todo \(i<m\),
Para un número \(k\), la regla \(k\)-NN para la clasificación binaria se define del siguiente modo:
input: muestra de entrenamiento \(S=(\boldsymbol{x}_{1}, y_{1}),\dots,(\boldsymbol{x}_{m}, y_{m})\)output: \(\forall~\boldsymbol{x}\in\mathcal{X}\), etiqueta mayoritaria en \(\{y_{\pi_{i}(\boldsymbol{x})}:~i\leq k\}\)
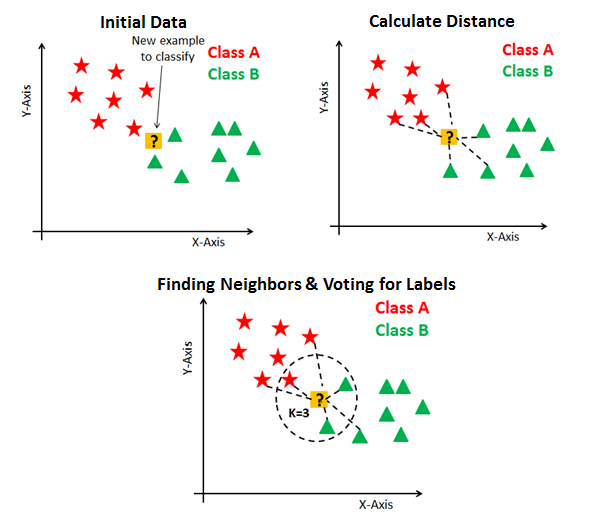
Fig. 2.1 Clasificación usando \(k\)-NN para \(k=3\). Source: kdnuggets.com.#
Desempate en la clasificación\(k\)-NN: En ocasiones ocurren empates a la hora de seleccionar la clase mayoritaria. Existen varias formas de abordar este problema, las siguientes son las más frecuentes.
1. Elija un \(k\) diferente
Nótese que, aunque un método de clasificación de tres vecinos más cercanos soluciona el problema de la selección de vecinos en las Fig. 2.2 i) y ii), el problema de la Fig. 2.2 iii) no es resuelto cuando se consideran por ejemplo cuatro. Elegir un \(k\) diferente, no siempre es la mejor solución.
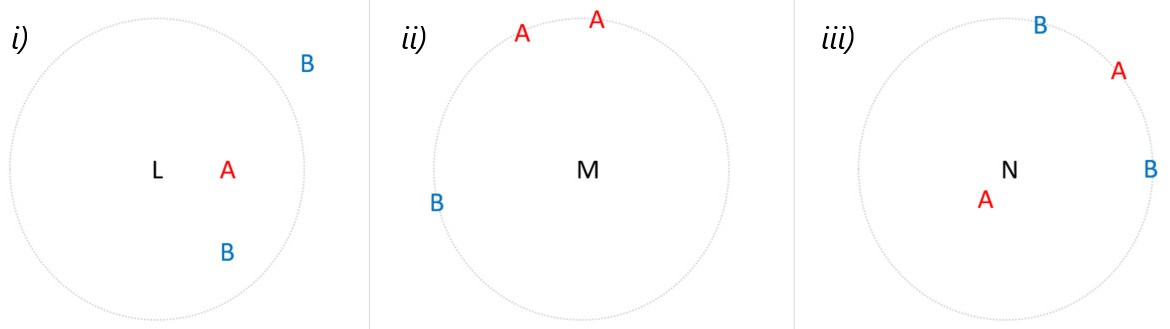
Fig. 2.2 k-NN: Empates respecto a distancia, en la selección de clase con mayor frecuencia.#
2. Elija al azar entre los valores empatados
Aplicando este enfoque a la Fig. 2.2 ii), cada una de las tres observaciones tendría la misma probabilidad de ser seleccionada como uno de los vecinos más cercanos.
En la Fig. 2.2 iii), se seleccionaría \(A\) como el vecino más cercano a \(N\), y uno de los tres puntos observados restantes se seleccionaría al azar.
Dependiendo de cuáles de los valores empatados se permitan en el modelo, podría tener un efecto significativo en cómo se clasifica \(N\).
3. Permitir observaciones hasta el punto de parada natural
La idea aquí es elegir el valor de \(k\geq 2\) más pequeño tal que, no existan empates
Para la Fig. 2.2 i), se seleccionarían las dos observaciones más cercanas, nótese que, para \(k=3\) se tiene un empate. Para la Fig. 2.2 ii), como hay un empate para \(k=3\), se consideran los tres vecinos más cercanos. La restricción de solo dos vecinos se elimina para esta observación en particular.
Del mismo modo, en la Fig. 2.2 iii) se seleccionan las cuatro observaciones. Observe que este método elegiría tantos valores como fuera necesario para evitar el empate. Si en la Fig. 2.2 ii) hubiera ocho puntos equidistantes, se incluirían los ocho en el modelo.
4. Con base en vecinos seleccionados
Supongamos que nos hemos decidido por el tercer método y que ya tenemos nuestros vecinos seleccionados
Elegir un\(k\)impar: Algunos sugieren simplemente elegir un valor impar para \(k\). Este método no siempre funciona, ya que los estados de clasificación también podrían ser impares \((A, B, C)\).Elegir al azar entre vecinos empatados. Con este método, \(L\) (considerando \(k=2\)) y \(N\) (considerando \(k=4\)) tienen la misma probabilidad de ser clasificados como \(A\) o \(B\). Pero, ¿es justo el azar? ¿Tiene sentido que \(N\), que está muy cerca de \(A\), tenga la misma probabilidad de ser \(B\)?Ponderación por distancia. Para resolver el problema planteado por el método anterior, es posible ponderar los vecinos de modo que los más cercanos al punto no observado tengan un “mayor voto”. Este método daría lugar a que tanto \(L\) como \(N\) se clasificaran como \(A\), ya que los vecinos \(A\) están más cerca que los demás en comparación.
Predictor: Definamos por \(h_{S}(\boldsymbol{x})\) la regla de predicción (el subíndice \(S\) hace hincapié en el hecho de que el predictor de salida depende de \(S\)). Esta función también se denomina predictor, hipótesis o clasificador. El predictor puede utilizarse para predecir la etiqueta de nuevos puntos de dominio. Cuando \(k=1\) (ver Definition 2.1), tenemos la regla \(1\)-NN:
Nótese que hemos considerado la métrica Euclideana en esta definición, pero, dependiendo del conjunto de datos, podría ser mas adecuado utilizar una métrica diferente (ver Manhatan, Minkowski). Esto es, una métrica alternativa, podría mejorar los errores cometidos por el clasificador.
Definition 2.2 (\(k\)-NN (Regresión))
Para problemas de regresión, a saber, \(\mathcal{Y}=\mathbb{R}\), se puede definir la regla de predicción como la media objetivo de los \(k\) vecinos más cercanos. Esto es,
Más en general, para alguna función \(\phi:~(\mathcal{X}, \mathcal{Y})^{k}\rightarrow\mathcal{Y}\), la regla \(k\)-NN con respecto a \(\phi\) es:
Se puede verificar que podemos lanzar la predicción por mayoría de etiquetas (clasificación) o por el objetivo promediado (regresión) como en la Ecuación (2.1) mediante una elección adecuada de \(\phi\).
La generalidad puede llevar a otras reglas, por ejemplo, si \(\mathcal{Y}=\mathbb{R}\), podemos tomar una media ponderada de los objetivos según la distancia a \(x\)
Definition 2.3 (Error empírico y verdadero revisado)
Para una distribución de probabilidad, \(\mathcal{D}\), sobre \(\mathcal{X}\times\mathcal{Y}\), se puede medir la probabilidad de que \(h\) cometa un error cuando los puntos etiquetados se extraen aleatoriamente según \(\mathcal{D}\). Redefinimos el error verdadero (o riesgo) de una regla de predicción \(h\) como
Minimización Empírica de Riesgo (ERM). Nos gustaría encontrar un predictor, \(h\), para el que se minimizara el error \(L_{\mathcal{D}}(h)\) sobre una clase de hipótesis denota por \(\mathcal{H}\), esto es: \(\text{ERM}_{\mathcal{H}}(S)\in\underset{h\in\mathcal{H}}{\text{argmin}}~L_{S}(h)\). Cada \(h\in\mathcal{H}\) es una función de \(\mathcal{X}\) a \(\mathcal{Y}\).Sin embargo, no se conocen los datos que generan \(\mathcal{D}\). A lo que sí se tiene acceso es a los datos de entrenamiento, \(S\). Una noción útil de error que puede calcular es el error de entrenamiento (riesgo empírico), es decir, el error en el que incurre el clasificador sobre la muestra de entrenamiento:
Dado \(S\), y un aprendizaje, se puede calcular \(L_{S}(h)\) para cualquier función \(h:X\rightarrow\{0,1\}\).
Deseamos encontrar alguna hipótesis, \(h : X\rightarrow Y\), que (probablemente de forma aproximada) minimice el riesgo verdadero,\(L_{D}(h)\).
Predictor óptimo de Bayes: Dada cualquier distribución de probabilidad \(\mathcal{D}\) sobre \(\mathcal{X}\times\{0, 1\}\), la mejor función de predicción de etiquetas de \(\mathcal{X}\) a \(\{0, 1\}\) será
Se puede verificar que para toda distribución de probabilidad \(\mathcal{D}\), el predictor óptimo de Bayes \(f_{D}\) es óptimo, en el sentido de que ningún otro clasificador, \(g : \mathcal \rightarrow\{0, 1\}\), tiene un error menor. Es decir, para cada clasificador \(g, L_{\mathcal{D}}(f_{\mathcal{D}}) \leq L_{\mathcal{D}}(g)\).
Definition 2.4 (Funciones de pérdidas generalizadas)
Dado cualquier conjunto \(\mathcal{H}\) (que desempeña el papel de nuestras hipótesis, o predictor) y algún dominio \(Z\) sea \(\ell\) cualquier función de \(\mathcal{H}\times Z\) al conjunto de los números reales no negativos, \(\ell: \mathcal{H}\times Z\rightarrow\mathbb{R}^{+}\). Llamamos a estas funciones, funciones de pérdida.
Nótese que para los problemas de predicción, tenemos que \(Z = \mathcal{X}\times\mathcal{Y}\). Sin embargo, nuestra noción de la función de pérdida se generaliza más allá de las tareas de predicción y, por tanto, permite que \(Z\) sea cualquier dominio de ejemplos.
Definimos ahora la función de riesgo como la pérdida esperada de un clasificador, \(h\in\mathcal{H}\), con respecto a la distribución de probabilidad \(\mathcal{D}\) sobre \(Z\), a saber,
Es decir, consideramos la esperanza de la pérdida de \(h\) sobre los objetos \(z\) elegidos aleatoriamente de acuerdo con \(\mathcal{D}\). Del mismo modo, definimos el riesgo empírico como la pérdida esperada sobre una muestra dada \(S=(z_{1},\dots,z_{m})\in Z^{m}\), a saber
Ejemplos: Dada una variable aleatoria \(z\) que abarca el conjunto de pares \(\mathcal{X}\times\mathcal{Y}\), definimos las siguientes funciones de pérdida
\(\ell_{\text{0-1}}(h, (x,y))\) se utiliza en problemas de clasificación binaria o multiclase. Hay que tener en cuenta que, para una variable aleatoria, \(\alpha\), que toma los valores \(\{0,1\}\),
\[\mathbb{E}_{\alpha\sim\mathcal{D}}[\alpha] = \mathbb{P}_{\alpha\sim\mathcal{D}}[\alpha = 1].\]Por lo tanto, las funciones de pérdida definidas en Eq. (2.4) y Eq. (2.2) son equivalentes.
Observation 2.1 (\(1\)-NN)
Dado que las reglas NN son métodos de aprendizaje tan naturales, sus propiedades de generalización han sido ampliamente estudiadas. La mayoría de los resultados anteriores son resultados de consistencia asintótica, que analizan el rendimiento de las reglas NN cuando el tamaño de la muestra, \(m\), tiende a \(\infty\), y la tasa de convergencia depende de la distribución subyacente.
Estamos interesados en aprendizajes de muestras de entrenamiento finitas y entender el rendimiento de generalización en función del tamaño de esos conjuntos de entrenamiento finitos y de supuestos previos claros sobre la distribución de los datos. Por lo tanto, presentamos un análisis de muestras finitas de la regla 1-NN.
Generalización de la regla \(1\)-NN
Ahora analizamos el error verdadero de la regla \(1\)-NN para la clasificación binaria con función pérdida \(0-1\) a saber, \(\mathcal{Y}=\{0, 1\}\) y \(\ell(h, (\boldsymbol{x}, y))=\mathbb{1}_{[h(\boldsymbol{x})\neq y]}\). También supondremos en todo el análisis que \(\mathcal{X} = [0,1]^{d}\) y \(\rho\) es la distancia euclidiana.
Empezaremos introduciendo algunas notaciones. Sea \(\mathcal{D}\) una distribución sobre \(\mathcal{X}\times\mathcal{Y}\). Denotemos por \(\mathcal{D}_{\mathcal{X}}\) la distribución marginal inducida por \(\mathcal{X}\) y sea \(\eta:\mathbb{R}^{d}\rightarrow\mathbb{R}\) la probabilidad condicional sobre las etiquetas, esto es,
La regla óptima de Bayes (es decir, la hipótesis que minimiza \(L_{\mathcal{D}}(h)\) sobre todas las funciones \(h\in\mathcal{H}\), ver Eq. (2.3)) es
Suponemos que la función de probabilidad condicional \(\eta\) es \(c\)-Lipschitz (ver Lipschitz continuity) para algún valor de \(c>0\). Es decir, \(\forall~\boldsymbol{x}, \boldsymbol{x}'\in\mathcal{X},~|\eta(\boldsymbol{x})-\eta(\boldsymbol{x}')|\leq c\|\boldsymbol{x}-\boldsymbol{x}'\|\). En otras palabras, esto significa que si dos vectores están próximos, es probable que sus etiquetas sean las mismas.
Nota
El siguiente Lema aplica la Lipschitzness de la función de probabilidad condicional para acotar el error verdadero de la regla 1-NN en función de la distancia entre cada instancia de prueba y su vecino más cercano en el conjunto de entrenamiento.
Lemma 2.1
Sea \(\mathcal{X}=[0,1]^{d},~ \mathcal{Y}=\{0,1\}\), y \(\mathcal{D}\) una distribución sobre \(\mathcal{X}\times\mathcal{Y}\), para la cual, la función de probabilidad condicional, \(\eta\), es una función \(c\)-Lipschitz. Sea \(S=(\boldsymbol{x}_{1}, y_{1}),\dots,(\boldsymbol{x}_{m}, y_{m})\) una muestra iid y sea \(h_{S}\) su correspondiente hipótesis \(1\)-NN. Sea \(h^{\star}\) la regla óptima de Bayes para \(\eta\). Entonces,
Demostración
Dado que \(L_{\mathcal{D}}(h_{S}):=\mathbb{E}_{(\boldsymbol{x}, y)\sim\mathcal{D}}(\ell(h, (\boldsymbol{x}, y)))=\mathbb{E}_{(\boldsymbol{x}, y)\sim\mathcal{D}}(\mathbb{1}_{[h(\boldsymbol{x})\neq y]})\), entonces \(\mathbb{E}(L_{\mathcal{D}}(h_{S})))\) es la probabilidad de muestrear un conjunto de entrenamiento \(S\) y un ejemplo adicional \((\boldsymbol{x}, y)\) tal que, la etiqueta de \(\boldsymbol{x}_{\pi_{1}(\boldsymbol{x})}\) es diferente de \(y\).
En otras palabras, podemos primero muestrear \(m\) ejemplos no etiquetados, \(S_{x}=(x_{1}, x_{2},\dots,x_{m})\), de acuerdo a \(\mathcal{D}_{x}\), y un nuevo ejemplo no etiquetado adicional, \(\boldsymbol{x}\sim\mathcal{D}_{x}\). Luego encontramos \(\boldsymbol{x}_{\pi_{1}(\boldsymbol{x})}\) que es el vecino mas cercano a \(\boldsymbol{x}\) en \(S_{\boldsymbol{x}}\), y finalmente muestrear: \(y\sim\eta(\boldsymbol{x})\) y \(y_{\pi_{1}(\boldsymbol{x})}\sim\eta(\boldsymbol{x}_{\pi_{1}(\boldsymbol{x})})\), donde \(\eta\) es la probabilidad condicional asociada a la distribución marginal sobre \(\mathcal{X},~\mathcal{D}_{x}\).
Entonces
Acotamos superiormente a: \(\underset{y\sim\eta(x), y_{\pi_{1}(x)}\sim\eta(\boldsymbol{x}_{\pi_{1}(\boldsymbol{x})})}{\mathbb{P}}(y\neq y_{\pi_{1}(\boldsymbol{x})}),~\forall~\boldsymbol{x}, \pi_{1}(\boldsymbol{x})\in\mathcal{D}\)
Definamos \(y':=y_{\pi_{1}(\boldsymbol{x})},~x':=\boldsymbol{x}_{\pi_{1}(\boldsymbol{x})}\)
Dado que \(\eta(\boldsymbol{x})=\mathbb{P}(y=1|\boldsymbol{x})\in[0, 1]\), entonces \(|2\eta(\boldsymbol{x})-1|\leq 1\). En efecto:
Dado que \(\eta(\boldsymbol{x})\) es \(c\)-Lipschitz, entonces, \(\forall~\boldsymbol{x},\boldsymbol{x}'\in\mathcal{X},~ |\eta(\boldsymbol{x})-\eta(\boldsymbol{x}')|\leq c\|\boldsymbol{x}-\boldsymbol{x}'\|\). Por lo tanto,
Reemplazando esta última desigualdad en (\(\star\)) se tiene que
Entonces
Dado que \(h^{\star}\) es la regla óptima de Bayes para \(\eta\), entonces \(h^{\star}\) minimiza la pérdida esperada del clasificador, esto es:
Nótese que la desigualdad anterior, que involucra el mínimo \(\min\{\eta(\boldsymbol{x}), 1-\eta(\boldsymbol{x})\}\), es valida. En efecto, si \(\eta(\boldsymbol{x})\in[0, 1]\) y \(\min\{\eta(\boldsymbol{x}), 1-\eta(\boldsymbol{x})\}=\eta(\boldsymbol{x})\), entonces \(\eta(\boldsymbol{x})\leq 1-\eta(\boldsymbol{x})\), por lo tanto:
Por lo tanto:
Observation
El siguiente paso es acotar la distancia entre una variable aleatoria \(\boldsymbol{x}\) y su vecino mas cercano en \(S\). Primero necesitaremos el siguiente Teorema, el cual acota el peso probabilístico de subconjuntos que no son alcanzados por una muestra aleatoria, como una función del tamaño de la muestra.
Lemma 2.2
Sea \(C_{1}, C_{2},\dots,C_{r}\) una colección de subconjuntos de algún dominio \(\mathcal{X}\). Sea \(S\) una sucesión de \(m\) puntos iid muestreados de acuerdo a una distribución de probabilidad \(\mathcal{D}\) sobre \(\mathcal{X}\). Entonces:
Demostración
Por linealidad del valor esperado se tiene que:
Entonces para cada \(i\), usando propiedades de independencia y complemento, dado que \(S\) es una sucesión de \(m\) puntos iid tenemos
Definamos \(\varepsilon=-\mathbb{P}(C_{i})\). Verifiquemos que \(e^{\varepsilon}\ge 1+\varepsilon,~\forall\varepsilon\in\mathbb{R}\). En efecto. Si \(~\varepsilon\leq-1\Rightarrow e^{\varepsilon}>0~\) y \(~1+\varepsilon\leq 0\Rightarrow 1+\varepsilon\leq0<e^{\varepsilon}\Rightarrow1+\varepsilon\leq e^{\varepsilon}\).
\[ \begin{align*} \text{Si}~\varepsilon>-1\Rightarrow e^{\varepsilon}&=\lim_{n\rightarrow\infty}\left(1+\frac{\varepsilon}{n}\right)^{n}\underset{\text{Bernoulli}}{\geq}\lim_{n\rightarrow\infty}1+n\frac{\varepsilon}{n}=1+\varepsilon. \end{align*} \]Entonces \(1+\varepsilon\leq e^{\varepsilon},~\forall\varepsilon\in\mathbb{R}\).
Definition 2.5 (Desigualdad de Bernoulli)
Desigualdad de Bernoulli: Sea \(x\in\mathbb{R}\) tal que \(x>-1\) y \(n\in\mathbb{Z}^{+}\), entonces, \((1+x)^{n}\geq1+nx\).
Dado que \(\varepsilon=-\mathbb{P}(C_{i})\), entonces
De este modo,
Theorem 2.1
Sea \(\mathcal{X}=[0, 1]^{d},~\mathcal{Y}=\{0, 1\}\) y \(\mathcal{D}\) una distribución sobre \(\mathcal{X}\times\mathcal{Y}\) para la cual la función de probabilidad condicional, \(\eta\), es una función \(c\)-Lipschitz. Denotamos con \(h_{S}\) el resultado de aplicar la regla \(1\)-NN a una muestra \(S\sim\mathcal{D}^{m}\). Entonces
Demostración
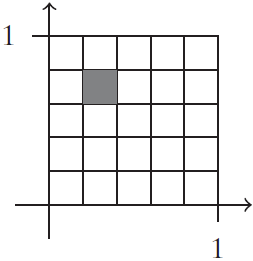
Fijemos \(\varepsilon=1/T\), para algún entero \(T\), sea \(r=T^{d}\), y sea \(C_{1}, C_{2}, \dots, C_{m}\) un cubrimiento del conjunto \(\mathcal{X}\) usando cajas de longitud \(\varepsilon\). Es decir, para cada \((\alpha_{1}, \alpha_{2},\dots,\alpha_{d})\in [T]^{d}\), existe un conjunto \(C_{i}\) de la forma
Entonces, \(\forall~\boldsymbol{x}, \boldsymbol{x}'\) en la misma caja \(\mathcal{B}_{x}\), se tiene que, \(x_{i}-x_{i}'\leq 1/T=\varepsilon\)
Si \(\boldsymbol{x}, \boldsymbol{x}'\) no caen en la misma caja \(\mathcal{B}_{x}\) entonces \(x_{i}-x_{i}'\leq 1,~\forall~i\), entonces \(\|\boldsymbol{x}-\boldsymbol{x}'\|\leq\sqrt{d}\).
Entonces, dado que \(\mathbb{P}\left(\bigcup_{C_{i}\cap S\neq\emptyset}C_{i}\right)\leq1\) y \(\boldsymbol{x}_{\pi_{1}(x)}\in S\)
Dado que \(r=T^{d}=(1/\varepsilon)^{d}=1/\varepsilon^{d}\), entonces:
Usando el Lemma 2.1 se tiene que
Finalmente, fijando \(\varepsilon=2m^{-1/(d+1)}\) se tiene que:
Entonces
Observation 2.2
El Teorema implica que si primero fijamos la distribución generadora de datos y luego hacemos tender \(m\) a infinito, entonces el error de la regla \(1\)-NN converge al doble del error de Bayes. El análisis puede generalizarse a valores mayores que \(k\), demostrando que el error esperado de la regla \(k\)-NN converge a \((1+\sqrt{8/k})\) veces el error del clasificador de Bayes.
2.2. Ejercicios#
En este ejercicio, demostrará el siguiente teorema para la regla \(k\)-NN.
Theorem 2.2
Sea \(\mathcal{X} = [0,1]^d\), \(\mathcal{Y} = \{0,1\}\) y \(D\) una distribución sobre \(\mathcal{X} \times \mathcal{Y}\) tal que la función de probabilidad condicional \(\eta\) es una función \(c\)-Lipschitz. Sea \(h_S\) el resultado de aplicar la regla de los \(k\)-vecinos más cercanos (\(k\)-NN) a una muestra \(S \sim \mathcal{D}^m\), donde \(k \geq 10\). Sea \(h^*\) la hipótesis óptima de Bayes. Entonces,
Parte 1: Demuestre el siguiente Lema
Lemma 2.3
Sea \(C_1, \dots, C_r\) una colección de subconjuntos de un conjunto dominio \(\mathcal{X}\). Sea \(S\) una secuencia de \(m\) puntos muestreados de manera independiente e idénticamente distribuida (i.i.d.) según alguna distribución de probabilidad \(\mathcal{D}\) sobre \(\mathcal{X}\). Entonces, para todo \(k \geq 2\), se cumple que:
\[ \mathbb{E}_{S \sim \mathcal{D}^m} \left[ \sum_{i : |C_i \cap S| < k} \mathbb{P}[C_i] \right] \leq \frac{2rk}{m}. \]
Sugerencia
Demostrar que
\[ \mathbb{E}\left[\sum_{i:|C_i \cap S| < k} \mathbb{P}[C_i]\right] = \sum_{i=1}^r \mathbb{P}[C_i] \mathbb{P}_S[|C_i \cap S| < k]. \]Fijar algún \(i\) y suponer que \(k < \mathbb{P}[C_i] m/2\). Usar el Lemma 2.5 para demostrar que
\[ \mathbb{P}_S[|C_i \cap S| < k] \leq \mathbb{P}_S\left[|C_i \cap S| < \mathbb{P}[C_i] m/2\right] \leq e^{-\mathbb{P}[C_i]m/8}. \]Usar la desigualdad \(\max_a a e^{-ma} \leq 1/me\) para demostrar que, para tal \(i\), tenemos
\[ \mathbb{P}[C_i] \mathbb{P}_S[|C_i \cap S| < k] \leq \mathbb{P}[C_i] e^{-\mathbb{P}[C_i]m/8} \leq \frac{8}{me}. \]Concluir la demostración utilizando el hecho de que, en el caso de \(k \geq \mathbb{P}[C_i]m/2\), claramente tenemos:
\[ \mathbb{P}[C_i] \mathbb{P}_S[|C_i \cap S| < k] \leq \mathbb{P}[C_i] \leq \frac{2k}{m}. \]
Parte 2: Utilizamos la notación \(y \sim p\) como una abreviatura para indicar que “\(y\) es una variable aleatoria de Bernoulli con valor esperado \(p\)”. Demuestre el siguiente lema:
Lemma 2.4
Sea \(k \geq 10\) y sean \(Z_1, \dots, Z_k\) variables aleatorias independientes de Bernoulli con \(\mathbb{P}[Z_i = 1] = p_i\). Denotemos por \(p = \frac{1}{k} \sum_{i} p_i\) y \(p' = \frac{1}{k} \sum_{i=1}^k Z_i\). Se debe demostrar que:
Sugerencia
Sin pérdida de generalidad, supongamos que \(p \leq 1/2\). Entonces, tenemos que \(\mathbb{P}_{y \sim p} [y \neq \mathbb{1}_{[p > 1/2]}] = p\). Definimos \(y^* = \mathbb{1}_{[p' > 1/2]}\).
A continuación, demuestre que:
Utilizando el Lemma 2.5, podemos demostrar que:
\[ \mathbb{P}[p' > 1/2] \leq e^{-k p h\left(\frac{1}{2p} - 1\right)}, \]donde \(h(a) = (1 + a) \log(1 + a) - a\).
Para concluir la demostración del lema, podemos apoyarnos en la siguiente desigualdad (sin necesidad de demostrarla): Para todo \(p \in [0, 1/2]\) y \(k \geq 10\):
Parte 3
Sea \(p, p' \in [0, 1]\) y \(y' \in \{0, 1\}\). Demuestre que:
Parte 4
Concluya la demostración del teorema de acuerdo con los siguientes pasos:
Tal como en la demostración del Theorem 2.1, sea \(\varepsilon > 0\) y sea \(\{C_1, \dots, C_r\}\) la cubierta del conjunto \(\mathcal{X}\) utilizando cajas de longitud \(\varepsilon\). Para cada par de puntos \(x, x' \in C_i\), tenemos que \(\|x - x'\| \leq \sqrt{d} \varepsilon\). En caso contrario, se cumple que \(\|x - x'\| \leq 2\sqrt{d}\).
Demostrar que
(2.5)#\[\begin{split} \begin{align*} \mathbb{E}_S[L_{\mathcal{D}}(h_S)] &\leq \mathbb{E}_S\left[\sum_{i : |C_i \cap S| < k} \mathbb{P}[C_i]\right] \\ &+ \max_i \mathbb{P}_S, (x, y)\left( h_S(x) \neq y \mid \forall j \in [k], \|x - x_{\pi_j(x)}\| \leq \varepsilon \sqrt{d} \right). \end{align*} \end{split}\]
Acotemos el primer sumando usando el Lemma 2.3.
Para acotar el segundo sumando, fijemos \(S|x\) y \(x\) de manera que todos los \(k\) vecinos de \(x\) en \(S|x\) estén a una distancia de a lo sumo \(\varepsilon\sqrt{d}\) de \(x\). Sin pérdida de generalidad, asumamos que los \(k\) vecinos más cercanos son \(x_1, \dots, x_k\). Denotemos \(p_i = \eta(x_i)\) y definamos \(p = \frac{1}{k} \sum_{i} p_i\). Utilizando el Ejercicio (2.5), mostramos que
Sin pérdida de generalidad, asumamos que \(p \leq 1/2\). Ahora, utilizamos el Lemma 2.4 para demostrar que
Además, se puede demostrar que
Combinando todos los resultados anteriores, obtenemos que el segundo sumando en la Ecuación (2.5) está acotado por
Usando \(r = (2/\epsilon)^{d}\), obtenemos
Finalmente, fijando \(\epsilon = 2m^{-1/(d+1)}\) y utilizando
\[ 6c m^{-1/(d+1)} \sqrt{d} + \frac{2k}{e} m^{-1/(d+1)} \leq \left( 6c \sqrt{d} + k \right) m^{-1/(d+1)}, \]se concluye la demostración.
Lemma 2.5 (Límite de Chernoff)
Sea \(Z_1, \dots, Z_m\) un conjunto de variables de Bernoulli independientes, donde para cada \(i\) se cumple que
Definimos \(p = \sum_{i=1}^{m} p_i\) y \(Z = \sum_{i=1}^{m} Z_i\). Entonces, para cualquier \(\delta > 0\), se tiene que
donde
2.3. Implementación#
Clasificación k-vecinos. Como ya se estudió anteriormente, en su versión más sencilla, el algoritmo k-NN solo considera exactamente un vecino más cercano, que es el dato de entrenamiento más cercano al punto para el que queremos hacer una predicción. La predicción es entonces simplemente la etiqueta conocida para este punto de entrenamiento.
import warnings
warnings.filterwarnings('ignore')
import mglearn
import matplotlib
mglearn.plots.plot_knn_classification(n_neighbors=1)
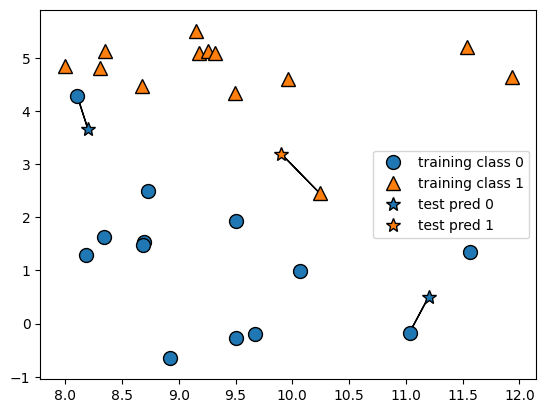
Se han añadido tres nuevos puntos de datos, mostrados como estrellas. Para cada uno de ellos, marcamos el punto más cercano en el conjunto de entrenamiento. La predicción del algoritmo del vecino más cercano es la etiqueta de ese punto (mostrada por el color de la cruz).
En lugar de considerar sólo al vecino más cercano, también podemos considerar un número arbitrario \(k\), de vecinos. De ahí viene el nombre del algoritmo \(k\)-vecinos más cercanos. Cuando se considera más de un vecino, se utiliza la votación para asignar una etiqueta. Esto significa que, para cada punto de prueba, contamos cuántos vecinos pertenecen a clase 0 y cuántos vecinos pertenecen a la clase 1. A continuación, asignamos la clase que es más frecuente: es decir, la clase mayoritaria entre los \(k\) vecinos más cercanos.
mglearn.plots.plot_knn_classification(n_neighbors=3)
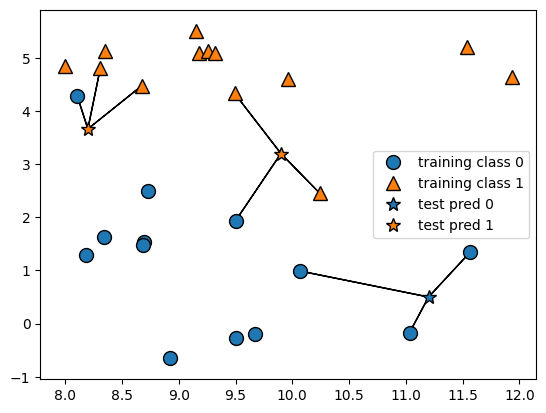
Aunque esta ilustración se refiere a un problema de clasificación binaria, este método puede aplicarse a conjuntos de datos con cualquier número de clases. Para más clases, contamos cuántos vecinos pertenecen a cada clase y volvemos a predecir la clase más común. Ahora veamos cómo podemos aplicar el algoritmo de los vecinos más cercanos utilizando
scikit-learn.En primer lugar, dividimos nuestros datos en un conjunto de entrenamiento y otro de prueba para poder evaluar el rendimiento de la generalización.
random_state=0nos asegura que obtendremos los mismos conjuntos de training y test para diferentes ejecuciones. Para mas información sobresklearn.model_selection.train_test_split(ver documentación train_test_split). Por defecto, cuando no es suministrado el porcentaje de entrenamientotrain_test_splitconsidera este porcentaje para el test como el 25%, esto estest_size=0.25
import numpy as np
import pandas as pd
import matplotlib
import matplotlib.pyplot as plt
from sklearn.datasets import load_breast_cancer
from sklearn.model_selection import train_test_split, cross_val_score, GridSearchCV
from sklearn.neighbors import KNeighborsClassifier
from sklearn.preprocessing import StandardScaler
from sklearn.pipeline import Pipeline
from sklearn.metrics import (classification_report, ConfusionMatrixDisplay,
RocCurveDisplay, roc_auc_score)
# Datos
cancer = load_breast_cancer()
X = pd.DataFrame(cancer.data, columns=cancer.feature_names)
y = pd.Series(cancer.target, name="diagnosis")
print("Balance de clases:")
print(y.value_counts().rename({0: "maligno", 1: "benigno"}))
print(f"Ratio: {y.value_counts(normalize=True).mul(100).round(1).to_dict()}\n")
# Split
X_train, X_test, y_train, y_test = train_test_split(
X, y, stratify=y, test_size=0.2, random_state=66
)
neighbors_settings = range(1, 21)
# MÉTODO A — Loop manual + cross_val_score (roc_auc)
train_accuracy, test_accuracy = [], []
train_auc, test_auc = [], []
cv_auc_scores = []
for n_neighbors in neighbors_settings:
pipe = Pipeline([
("scaler", StandardScaler()),
("knn", KNeighborsClassifier(n_neighbors=n_neighbors))
])
cv_auc = cross_val_score(pipe, X_train, y_train, cv=5, scoring="roc_auc")
cv_auc_scores.append(cv_auc.mean())
pipe.fit(X_train, y_train)
train_accuracy.append(pipe.score(X_train, y_train))
test_accuracy.append(pipe.score(X_test, y_test))
train_auc.append(roc_auc_score(y_train, pipe.predict_proba(X_train)[:, 1]))
test_auc.append(roc_auc_score(y_test, pipe.predict_proba(X_test)[:, 1]))
best_k_manual = list(neighbors_settings)[np.argmax(cv_auc_scores)]
# MÉTODO B — GridSearchCV (roc_auc)
pipe_grid = Pipeline([
("scaler", StandardScaler()),
("knn", KNeighborsClassifier())
])
param_grid = {"knn__n_neighbors": list(neighbors_settings)}
grid_search = GridSearchCV(
pipe_grid,
param_grid,
cv=5,
scoring="roc_auc",
return_train_score=True
)
grid_search.fit(X_train, y_train)
best_k_grid = grid_search.best_params_["knn__n_neighbors"]
cv_auc_grid = grid_search.cv_results_["mean_test_score"]
# Comparación
print("=" * 56)
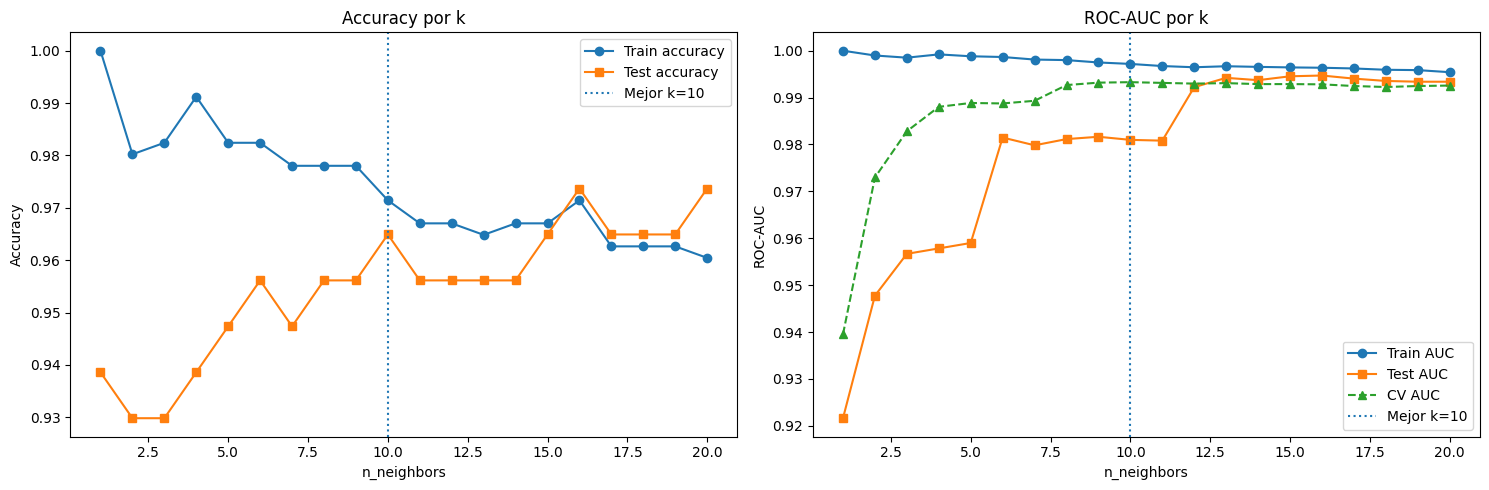
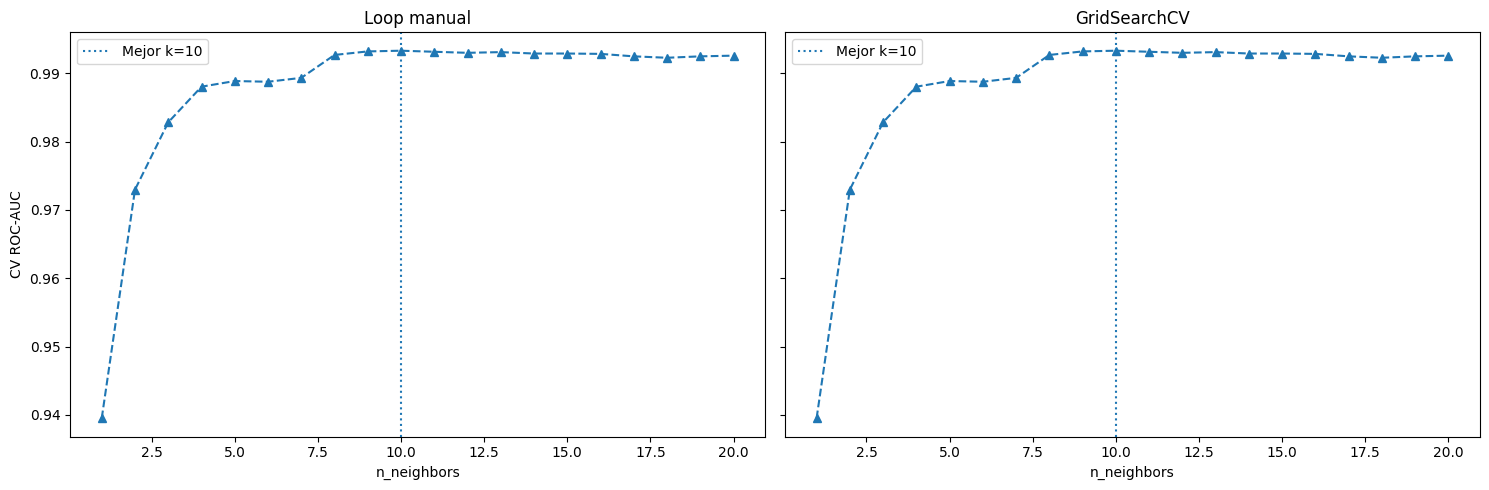
print(f"Mejor k — Manual loop : {best_k_manual} (CV AUC: {max(cv_auc_scores):.6f})")
print(f"Mejor k — GridSearchCV: {best_k_grid} (CV AUC: {grid_search.best_score_:.6f})")
print("-" * 56)
print(f"¿CV AUC scores idénticos? {np.allclose(cv_auc_scores, cv_auc_grid, atol=1e-10)}")
print("=" * 56)
# Figura 1 — Accuracy vs AUC
matplotlib.rc_file_defaults()
fig, axes = plt.subplots(1, 2, figsize=(15, 5))
ax = axes[0]
ax.plot(neighbors_settings, train_accuracy, label="Train accuracy", marker="o")
ax.plot(neighbors_settings, test_accuracy, label="Test accuracy", marker="s")
ax.axvline(best_k_manual, linestyle=":", label=f"Mejor k={best_k_manual}")
ax.set_title("Accuracy por k")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("Accuracy")
ax.legend()
ax = axes[1]
ax.plot(neighbors_settings, train_auc, label="Train AUC", marker="o")
ax.plot(neighbors_settings, test_auc, label="Test AUC", marker="s")
ax.plot(neighbors_settings, cv_auc_scores, label="CV AUC", marker="^", linestyle="--")
ax.axvline(best_k_manual, linestyle=":", label=f"Mejor k={best_k_manual}")
ax.set_title("ROC-AUC por k")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("ROC-AUC")
ax.legend()
plt.tight_layout()
plt.show()
# Figura 2 — Loop vs GridSearchCV
fig, axes = plt.subplots(1, 2, figsize=(15, 5), sharey=True)
ax = axes[0]
ax.plot(neighbors_settings, cv_auc_scores, marker="^", linestyle="--")
ax.axvline(best_k_manual, linestyle=":", label=f"Mejor k={best_k_manual}")
ax.set_title("Loop manual")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("CV ROC-AUC")
ax.legend()
ax = axes[1]
ax.plot(neighbors_settings, cv_auc_grid, marker="^", linestyle="--")
ax.axvline(best_k_grid, linestyle=":", label=f"Mejor k={best_k_grid}")
ax.set_title("GridSearchCV")
ax.set_xlabel("n_neighbors")
ax.legend()
plt.tight_layout()
plt.show()
# Figura 3 — ROC y matriz de confusión
fig, axes = plt.subplots(1, 2, figsize=(13, 5))
RocCurveDisplay.from_estimator(
grid_search.best_estimator_,
X_test,
y_test,
ax=axes[0]
)
axes[0].plot([0, 1], [0, 1], "k--")
axes[0].set_title(f"Curva ROC — k={best_k_grid}")
ConfusionMatrixDisplay.from_estimator(
grid_search.best_estimator_,
X_test,
y_test,
display_labels=cancer.target_names,
ax=axes[1]
)
axes[1].set_title(f"Matriz de confusión — k={best_k_grid}")
plt.tight_layout()
plt.show()
# Reporte final
y_pred = grid_search.predict(X_test)
y_proba = grid_search.predict_proba(X_test)[:, 1]
final_auc = roc_auc_score(y_test, y_proba)
print(f"\nReporte final — k={best_k_grid} | Test ROC-AUC: {final_auc:.4f}")
print(classification_report(y_test, y_pred, target_names=cancer.target_names))
Balance de clases:
diagnosis
benigno 357
maligno 212
Name: count, dtype: int64
Ratio: {1: 62.7, 0: 37.3}
========================================================
Mejor k — Manual loop : 10 (CV AUC: 0.993292)
Mejor k — GridSearchCV: 10 (CV AUC: 0.993292)
--------------------------------------------------------
¿CV AUC scores idénticos? True
========================================================
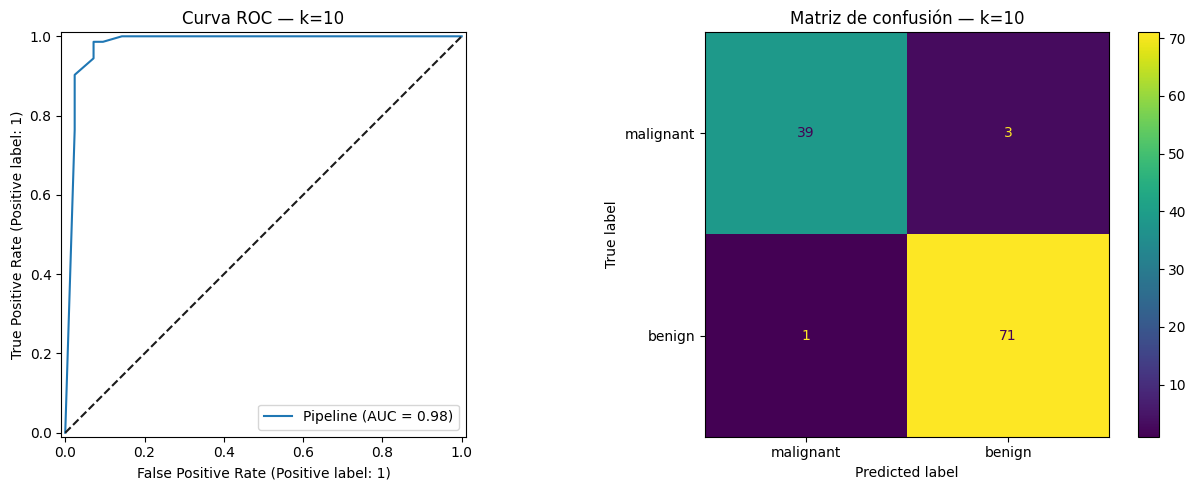
Reporte final — k=10 | Test ROC-AUC: 0.9810
precision recall f1-score support
malignant 0.97 0.93 0.95 42
benign 0.96 0.99 0.97 72
accuracy 0.96 114
macro avg 0.97 0.96 0.96 114
weighted avg 0.97 0.96 0.96 114
La comparación entre loop manual con
cross_validateyGridSearchCV, ambos con CV-5 yscoring="roc_auc", produjo scores matemáticamente idénticos (np.allclose = True), confirmando queGridSearchCVes una abstracción eficiente del mismo proceso con refit automático incluido.El
PipelineconStandardScalereliminó la fuga de datos al ajustar la estandarización solo sobre train en cada fold, condición crítica en KNN dado que sus predicciones dependen de distancias euclidianas. El diagnóstico de sobreajuste combinó la brecha train−val por k,ttest_1samppara verificar si es estadísticamente distinta de cero, y un t-test pareado entre k=1 y k óptimo. Con solo 26 observaciones y 7 en test, el CV-5 es la única estrategia estadísticamente defensible para estimar generalización.ROC-AUC se prefirió sobre accuracy por evaluar la capacidad discriminativa en todos los umbrales posibles, manteniéndose informativa ante desbalance de clases, condición frecuente en aplicaciones reales como medicina, detección de fraude o riesgo crediticio.
2.4. Análisis de KNeighborsClassifier#
Para los conjuntos de datos bidimensionales, también podemos ilustrar la predicción para todos los posibles puntos de prueba en el plano \(xy\). Coloreamos el plano según la clase que se asignaría a un punto en esta región. Esto nos permite ver el límite de decisión (decision boundary) (ver plot_2d_separator), el cual está entre el lugar donde el algoritmo asigna la clase 0 y el lugar donde asigna la clase 1.
import matplotlib.pyplot as plt
# Seleccionar solo dos características para visualización 2D
X_2d = X.iloc[:, :2].values # mean radius y mean texture
y_2d = y.values
# Escalar las características para mejor visualización
scaler_2d = StandardScaler()
X_2d_scaled = scaler_2d.fit_transform(X_2d)
# Definir 9 valores diferentes de k (vecinos)
neighbors_values = [1, 2, 3, 5, 7, 9, 11, 15, 20]
# Crear la figura con 3x3 subplots (9 subplots en total)
fig, axes = plt.subplots(3, 3, figsize=(15, 12))
axes = axes.ravel() # Aplanar para iterar fácilmente
for idx, n_neighbors in enumerate(neighbors_values):
ax = axes[idx]
# Entrenar clasificador con los datos 2D escalados
clf = KNeighborsClassifier(n_neighbors=n_neighbors)
clf.fit(X_2d_scaled, y_2d)
# Graficar frontera de decisión (requiere mglearn)
try:
import mglearn
mglearn.plots.plot_2d_separator(
clf, X_2d_scaled, fill=True, eps=0.5, ax=ax, alpha=0.4
)
except ImportError:
# Alternativa manual si mglearn no está instalado
from matplotlib.colors import ListedColormap
import numpy as np
h = 0.02 # paso de la malla
x_min, x_max = X_2d_scaled[:, 0].min() - 0.5, X_2d_scaled[:, 0].max() + 0.5
y_min, y_max = X_2d_scaled[:, 1].min() - 0.5, X_2d_scaled[:, 1].max() + 0.5
xx, yy = np.meshgrid(np.arange(x_min, x_max, h),
np.arange(y_min, y_max, h))
Z = clf.predict(np.c_[xx.ravel(), yy.ravel()])
Z = Z.reshape(xx.shape)
cmap_light = ListedColormap(['#FFAAAA', '#AAFFAA'])
ax.contourf(xx, yy, Z, alpha=0.4, cmap=cmap_light)
# Graficar puntos
try:
import mglearn
scatter = mglearn.discrete_scatter(X_2d_scaled[:, 0], X_2d_scaled[:, 1], y_2d, ax=ax)
except:
# Alternativa manual
for class_idx, color, label in zip([0, 1], ['red', 'green'], ['Maligno', 'Benigno']):
ax.scatter(X_2d_scaled[y_2d == class_idx, 0],
X_2d_scaled[y_2d == class_idx, 1],
c=color, label=label, edgecolor='black', s=30, alpha=0.7)
# Configurar el subplot
ax.set_title(f"k = {n_neighbors} vecino(s)", fontsize=11)
ax.set_xlabel("Mean radius (escalado)", fontsize=9)
ax.set_ylabel("Mean texture (escalado)", fontsize=9)
ax.set_xlim(X_2d_scaled[:, 0].min() - 0.5, X_2d_scaled[:, 0].max() + 0.5)
ax.set_ylim(X_2d_scaled[:, 1].min() - 0.5, X_2d_scaled[:, 1].max() + 0.5)
# Añadir leyenda en el primer subplot (esquina inferior derecha)
try:
axes[0].legend(['Maligno', 'Benigno'], loc='lower right', fontsize=8)
except:
pass
# Título general
plt.suptitle("Fronteras de decisión de k-NN con diferentes valores de k",
fontsize=14, fontweight='bold')
plt.tight_layout()
plt.show()
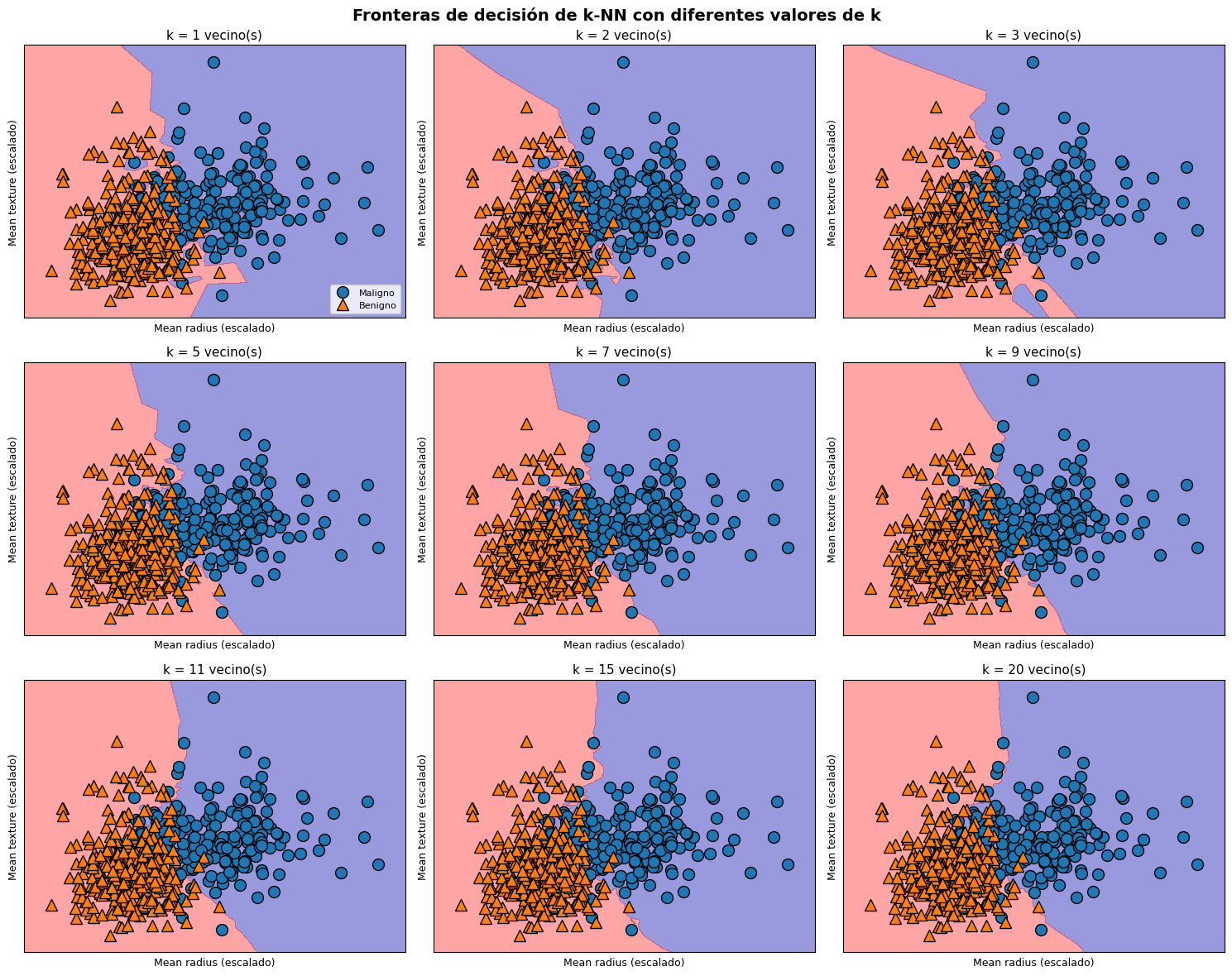
De acuerdo con la figura, se observa que cuando \(k\) es pequeño (por ejemplo, \(k = 1\)), la frontera de decisión es altamente irregular y se ajusta muy de cerca a los datos de entrenamiento, capturando incluso variaciones locales y ruido. A medida que aumenta el número de vecinos, la frontera de decisión se vuelve progresivamente más suave y estable, reflejando un modelo menos sensible a fluctuaciones individuales de los datos.
En este sentido, valores pequeños de \(k\) están asociados a modelos de alta complejidad (bajo sesgo y alta varianza), mientras que valores grandes de \(k\) producen modelos más simples (mayor sesgo y menor varianza), con fronteras de decisión más generales.
En el caso extremo en que \(k\) es igual al número total de observaciones del conjunto de entrenamiento, todos los puntos tendrían los mismos vecinos, lo que implica que el modelo asignaría siempre la misma clase a cualquier nueva observación, correspondiente a la clase mayoritaria del conjunto de datos.
2.5. Aplicación: Breast Cancer Dataset#
Breast Cancer Dataset. Investiguemos si podemos confirmar la conexión entre la complejidad del modelo y la generalización que hemos discutido antes. Lo haremos con el conjunto de datos de cáncer de mama (Breast Cancer) del mundo real.
2.6. Análisis Exploratorio de Datos#
Procedemos a realizar un análisis exploratorio de datos para investigar y resumir principales características de nuestros datos. Primero cargamos nuestro dataset usando la función
load_breast_cancer()desklearn.datasets
from sklearn.datasets import load_breast_cancer
cancer = load_breast_cancer()
list(cancer.target_names)
['malignant', 'benign']
list(cancer.feature_names)
['mean radius',
'mean texture',
'mean perimeter',
'mean area',
'mean smoothness',
'mean compactness',
'mean concavity',
'mean concave points',
'mean symmetry',
'mean fractal dimension',
'radius error',
'texture error',
'perimeter error',
'area error',
'smoothness error',
'compactness error',
'concavity error',
'concave points error',
'symmetry error',
'fractal dimension error',
'worst radius',
'worst texture',
'worst perimeter',
'worst area',
'worst smoothness',
'worst compactness',
'worst concavity',
'worst concave points',
'worst symmetry',
'worst fractal dimension']
cancer.data.shape
(569, 30)
cancer.target.shape
(569,)
import pandas as pd
df = pd.DataFrame(cancer.data, columns = cancer.feature_names)
df.insert(0, 'diagnosis', cancer.target)
df.head()
| diagnosis | mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 0 | 17.99 | 10.38 | 122.80 | 1001.0 | 0.11840 | 0.27760 | 0.3001 | 0.14710 | 0.2419 | ... | 25.38 | 17.33 | 184.60 | 2019.0 | 0.1622 | 0.6656 | 0.7119 | 0.2654 | 0.4601 | 0.11890 |
| 1 | 0 | 20.57 | 17.77 | 132.90 | 1326.0 | 0.08474 | 0.07864 | 0.0869 | 0.07017 | 0.1812 | ... | 24.99 | 23.41 | 158.80 | 1956.0 | 0.1238 | 0.1866 | 0.2416 | 0.1860 | 0.2750 | 0.08902 |
| 2 | 0 | 19.69 | 21.25 | 130.00 | 1203.0 | 0.10960 | 0.15990 | 0.1974 | 0.12790 | 0.2069 | ... | 23.57 | 25.53 | 152.50 | 1709.0 | 0.1444 | 0.4245 | 0.4504 | 0.2430 | 0.3613 | 0.08758 |
| 3 | 0 | 11.42 | 20.38 | 77.58 | 386.1 | 0.14250 | 0.28390 | 0.2414 | 0.10520 | 0.2597 | ... | 14.91 | 26.50 | 98.87 | 567.7 | 0.2098 | 0.8663 | 0.6869 | 0.2575 | 0.6638 | 0.17300 |
| 4 | 0 | 20.29 | 14.34 | 135.10 | 1297.0 | 0.10030 | 0.13280 | 0.1980 | 0.10430 | 0.1809 | ... | 22.54 | 16.67 | 152.20 | 1575.0 | 0.1374 | 0.2050 | 0.4000 | 0.1625 | 0.2364 | 0.07678 |
5 rows × 31 columns
df_copy = df.copy()
Aquí
0=malignant, 1=benign. Verifiquemos que tipos de datos contiene el dataset. La funcióninfo()proporciona información sobre los tipos de datos, columnas, recuento de valores nulos, uso de memoria, etc.
df.info()
<class 'pandas.core.frame.DataFrame'>
RangeIndex: 569 entries, 0 to 568
Data columns (total 31 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 diagnosis 569 non-null int64
1 mean radius 569 non-null float64
2 mean texture 569 non-null float64
3 mean perimeter 569 non-null float64
4 mean area 569 non-null float64
5 mean smoothness 569 non-null float64
6 mean compactness 569 non-null float64
7 mean concavity 569 non-null float64
8 mean concave points 569 non-null float64
9 mean symmetry 569 non-null float64
10 mean fractal dimension 569 non-null float64
11 radius error 569 non-null float64
12 texture error 569 non-null float64
13 perimeter error 569 non-null float64
14 area error 569 non-null float64
15 smoothness error 569 non-null float64
16 compactness error 569 non-null float64
17 concavity error 569 non-null float64
18 concave points error 569 non-null float64
19 symmetry error 569 non-null float64
20 fractal dimension error 569 non-null float64
21 worst radius 569 non-null float64
22 worst texture 569 non-null float64
23 worst perimeter 569 non-null float64
24 worst area 569 non-null float64
25 worst smoothness 569 non-null float64
26 worst compactness 569 non-null float64
27 worst concavity 569 non-null float64
28 worst concave points 569 non-null float64
29 worst symmetry 569 non-null float64
30 worst fractal dimension 569 non-null float64
dtypes: float64(30), int64(1)
memory usage: 137.9 KB
El método
DataFrame.describe()genera estadísticos descriptivos que resumen tendencia central, dispersión y la forma de la distribución de un conjunto de datos, excluyendo los valoresNaN. Una cosa importante es que el método describe() sólo trabaja con valores numéricos. Por lo tanto, si hay algún valor categórico en una columna, el método describe() lo ignorará y mostrará el resumen de las demás columnas, a menos que se pase elparámetro include="all".
df.describe()
| diagnosis | mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| count | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | ... | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 |
| mean | 0.627417 | 14.127292 | 19.289649 | 91.969033 | 654.889104 | 0.096360 | 0.104341 | 0.088799 | 0.048919 | 0.181162 | ... | 16.269190 | 25.677223 | 107.261213 | 880.583128 | 0.132369 | 0.254265 | 0.272188 | 0.114606 | 0.290076 | 0.083946 |
| std | 0.483918 | 3.524049 | 4.301036 | 24.298981 | 351.914129 | 0.014064 | 0.052813 | 0.079720 | 0.038803 | 0.027414 | ... | 4.833242 | 6.146258 | 33.602542 | 569.356993 | 0.022832 | 0.157336 | 0.208624 | 0.065732 | 0.061867 | 0.018061 |
| min | 0.000000 | 6.981000 | 9.710000 | 43.790000 | 143.500000 | 0.052630 | 0.019380 | 0.000000 | 0.000000 | 0.106000 | ... | 7.930000 | 12.020000 | 50.410000 | 185.200000 | 0.071170 | 0.027290 | 0.000000 | 0.000000 | 0.156500 | 0.055040 |
| 25% | 0.000000 | 11.700000 | 16.170000 | 75.170000 | 420.300000 | 0.086370 | 0.064920 | 0.029560 | 0.020310 | 0.161900 | ... | 13.010000 | 21.080000 | 84.110000 | 515.300000 | 0.116600 | 0.147200 | 0.114500 | 0.064930 | 0.250400 | 0.071460 |
| 50% | 1.000000 | 13.370000 | 18.840000 | 86.240000 | 551.100000 | 0.095870 | 0.092630 | 0.061540 | 0.033500 | 0.179200 | ... | 14.970000 | 25.410000 | 97.660000 | 686.500000 | 0.131300 | 0.211900 | 0.226700 | 0.099930 | 0.282200 | 0.080040 |
| 75% | 1.000000 | 15.780000 | 21.800000 | 104.100000 | 782.700000 | 0.105300 | 0.130400 | 0.130700 | 0.074000 | 0.195700 | ... | 18.790000 | 29.720000 | 125.400000 | 1084.000000 | 0.146000 | 0.339100 | 0.382900 | 0.161400 | 0.317900 | 0.092080 |
| max | 1.000000 | 28.110000 | 39.280000 | 188.500000 | 2501.000000 | 0.163400 | 0.345400 | 0.426800 | 0.201200 | 0.304000 | ... | 36.040000 | 49.540000 | 251.200000 | 4254.000000 | 0.222600 | 1.058000 | 1.252000 | 0.291000 | 0.663800 | 0.207500 |
8 rows × 31 columns
Realicemos tabla de frecuencias y diagrama de barras para nuestra variable respuesta
df.diagnosis.value_counts()
diagnosis
1 357
0 212
Name: count, dtype: int64
import seaborn as sns
sns.set_style("whitegrid")
plt.title('Count of cancer type')
sns.countplot(x=df.diagnosis)
plt.xlabel('Diagnosis')
plt.ylabel('Frequency')
plt.show()
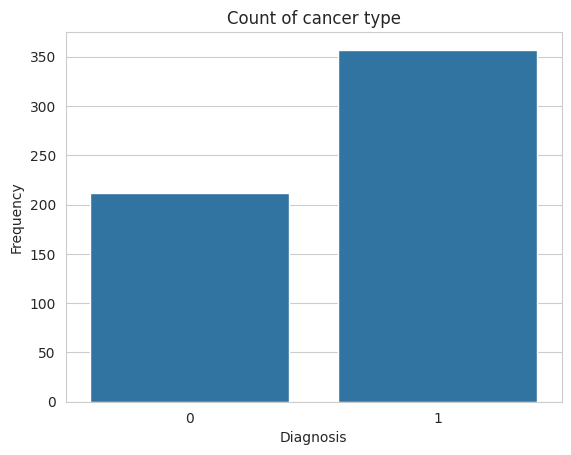
Nótese que nuestro dataset está desbalanceado. Existen técnicas como SMOTE y Stratified sampling, que pueden utilizarse para mejorar el score de clasificación de datos desbalanceados. Utilícela en su proyecto final de investigación. Verifiquemos además si existen datos faltantes en nuestro
Dataframe
df.isnull().sum()
diagnosis 0
mean radius 0
mean texture 0
mean perimeter 0
mean area 0
mean smoothness 0
mean compactness 0
mean concavity 0
mean concave points 0
mean symmetry 0
mean fractal dimension 0
radius error 0
texture error 0
perimeter error 0
area error 0
smoothness error 0
compactness error 0
concavity error 0
concave points error 0
symmetry error 0
fractal dimension error 0
worst radius 0
worst texture 0
worst perimeter 0
worst area 0
worst smoothness 0
worst compactness 0
worst concavity 0
worst concave points 0
worst symmetry 0
worst fractal dimension 0
dtype: int64
Seleccionamos aquellas variables que están correlacionadas con la variable respuesta usando: The Point Biserial Coefficient of Correlation. Para que este método sea efectivo, requiere que las variables explicativas se distribuyan normalmente. Usamos una transformación en el caso que sea necesario
from scipy.stats import pointbiserialr, kstest, norm
from sklearn.preprocessing import StandardScaler
scaler = StandardScaler()
scaler_params = {}
significant_columns = ['diagnosis']
for column in df.columns[1:]:
D, p_value = kstest(df[column], norm.cdf, args=(df[column].mean(), df[column].std()))
if p_value < 0.05:
scaler.fit(df[column].values.reshape(-1, 1))
scaler_params[column] = (scaler.mean_, scaler.scale_) # Guardar la media y la desviación estándar
df[column] = scaler.transform(df[column].values.reshape(-1, 1))
corr, p_value = pointbiserialr(df[column], df['diagnosis'])
if p_value < 0.05:
significant_columns.append(column)
df_significant = df[significant_columns]
for column, (mean, scale) in scaler_params.items():
if column in df_significant.columns: # Solo revertir las columnas que están en df_significant
df_significant[column] = df_significant[column] * scale + mean # Revertir la normalización
print("\nDataFrame con las columnas significativas y revertidas a su escala original:")
df = df_significant
df.head()
DataFrame con las columnas significativas y revertidas a su escala original:
| diagnosis | mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 0 | 17.99 | 10.38 | 122.80 | 1001.0 | 0.11840 | 0.27760 | 0.3001 | 0.14710 | 0.2419 | ... | 25.38 | 17.33 | 184.60 | 2019.0 | 0.1622 | 0.6656 | 0.7119 | 0.2654 | 0.4601 | 0.11890 |
| 1 | 0 | 20.57 | 17.77 | 132.90 | 1326.0 | 0.08474 | 0.07864 | 0.0869 | 0.07017 | 0.1812 | ... | 24.99 | 23.41 | 158.80 | 1956.0 | 0.1238 | 0.1866 | 0.2416 | 0.1860 | 0.2750 | 0.08902 |
| 2 | 0 | 19.69 | 21.25 | 130.00 | 1203.0 | 0.10960 | 0.15990 | 0.1974 | 0.12790 | 0.2069 | ... | 23.57 | 25.53 | 152.50 | 1709.0 | 0.1444 | 0.4245 | 0.4504 | 0.2430 | 0.3613 | 0.08758 |
| 3 | 0 | 11.42 | 20.38 | 77.58 | 386.1 | 0.14250 | 0.28390 | 0.2414 | 0.10520 | 0.2597 | ... | 14.91 | 26.50 | 98.87 | 567.7 | 0.2098 | 0.8663 | 0.6869 | 0.2575 | 0.6638 | 0.17300 |
| 4 | 0 | 20.29 | 14.34 | 135.10 | 1297.0 | 0.10030 | 0.13280 | 0.1980 | 0.10430 | 0.1809 | ... | 22.54 | 16.67 | 152.20 | 1575.0 | 0.1374 | 0.2050 | 0.4000 | 0.1625 | 0.2364 | 0.07678 |
5 rows × 26 columns
Pasamos a verficar si existe correlación entre las características. En caso positivo, removemos multicolinealidad usando el Variance Inflation Factor
corr = df.iloc[: , 1:].corr()
corr.shape
(25, 25)
import numpy as np
mask = np.zeros_like(corr)
mask[np.triu_indices_from(mask)] = True
sns.set(font_scale=1.8)
plt.figure(figsize=(20,20))
sns.heatmap(corr, mask=mask, cbar=True, fmt='.1f', annot=True, annot_kws={'size':15}, cmap='Reds');
Trazamos histogramas de cada característica en nuestro dataset
melted_data = pd.melt(df, id_vars = "diagnosis",value_vars = ['mean radius', 'mean texture',
'mean perimeter'])
sns.set(font_scale=1.8)
plt.figure(figsize = (20,10))
sns.boxplot(x = "value", y = "variable", hue="diagnosis",data= melted_data);
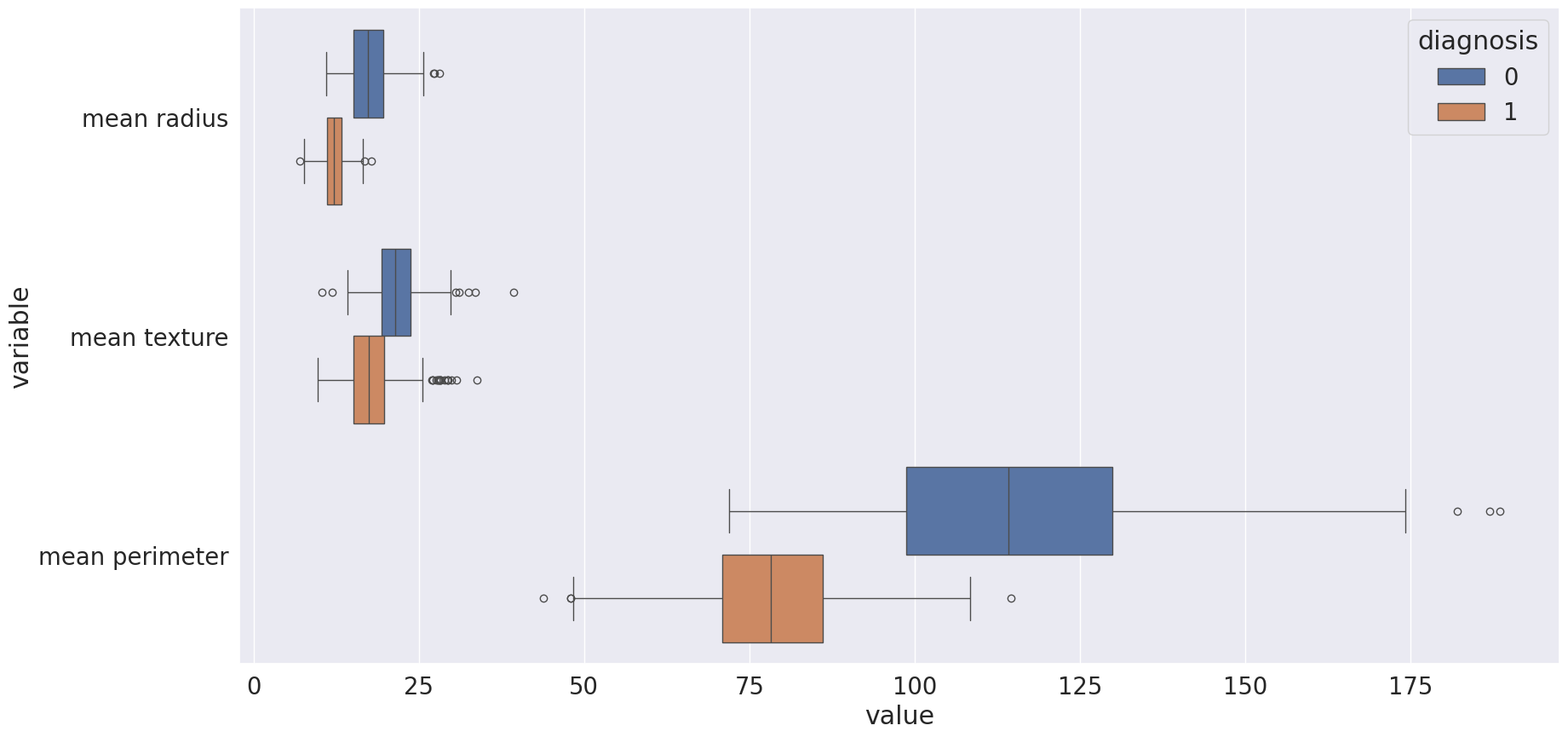
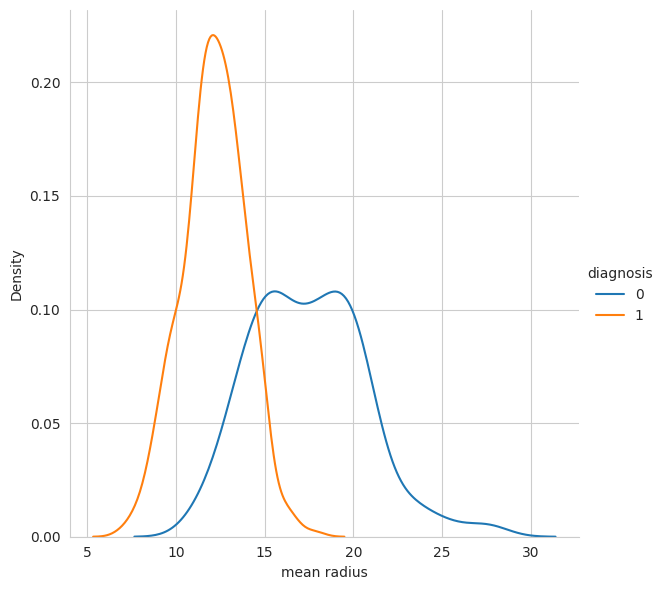
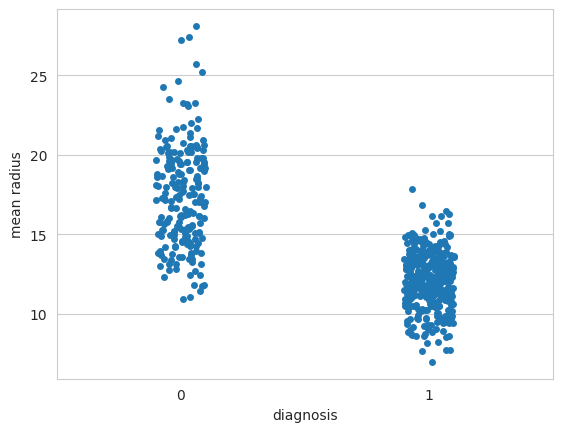
Diagrama de densidad de distribución KDE y distribución mediante el diagrama de dispersión
stripplot()
matplotlib.rc_file_defaults()
sns.set_style("whitegrid")
sns.FacetGrid(df, hue="diagnosis", height=6).map(sns.kdeplot, "mean radius").add_legend();
sns.stripplot(x="diagnosis", y="mean radius", data=df, jitter=True, edgecolor="gray");
¿Debo siempre eliminar variables explicativas no correlacionadas con mi variable respuesta?
No es obligatorio eliminar variables sin correlación con la variable respuesta. La correlación mide solo relaciones lineales, y algunas variables pueden ser útiles en modelos no lineales. Además, algoritmos como Lasso, Random Forest o Gradient Boosting, SVM, ANNs manejan variables irrelevantes automáticamente.
Eliminar prematuramente puede descartar información valiosa. Sin embargo, un análisis de importancia de características sigue siendo recomendable para mejorar eficiencia y evitar ruido innecesario. En su lugar, es mejor aplicar técnicas como SHAP, Permutation Importance, RFE o transformaciones como PCA para evaluar la relevancia de las variables antes de eliminarlas.
2.6.1. Multicolinealidad#
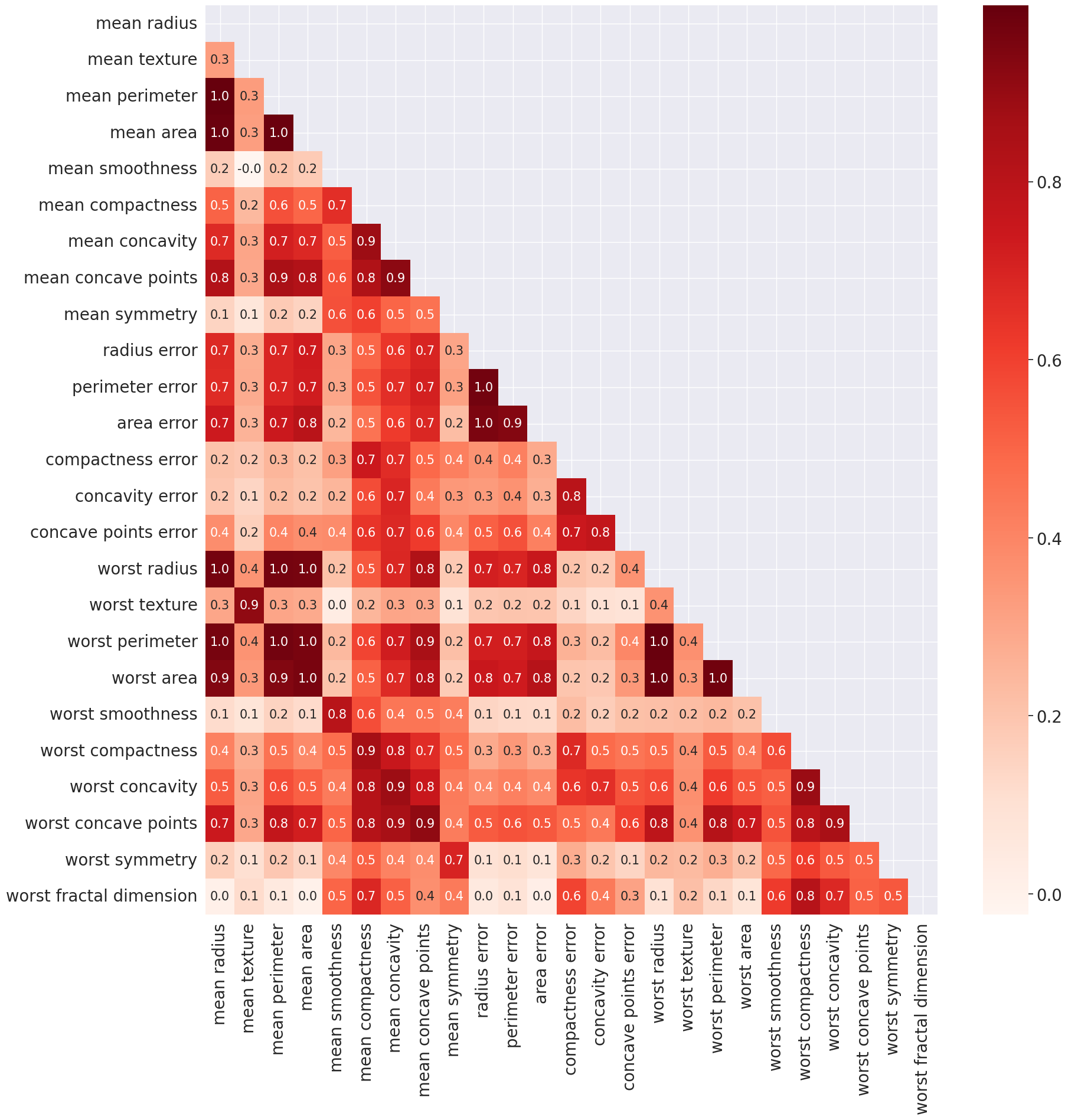
La multicolinealidad es un problema ya que, reduce la importancia de las variables independientes. A fin de solucionar este problema, se eliminan los predictores altamente correlacionados. Podemos comprobar la presencia de multicolinealidad entre algunas de las variables. Por ejemplo, la columna mean radius tiene una correlación de 1.0 con las columnas mean perimeter y mean área, respectivamente. Esto se debe a que las tres columnas contienen esencialmente la misma información, que es el tamaño físico de la observación.
Por lo tanto, sólo debemos elegir una de las tres columnas cuando pasemos al análisis posterior. Otro lugar donde la multicolinealidad es evidente, es entre las columnas
"mean"y"worst". Por ejemplo, la columnamean radiustiene una correlación de 1.0 con la columnaworst radius. También hay multicolinealidad entre los atributoscompactness, concavityyconcave points. Así que podemos elegir solo uno de estos, por ejemplocompactness. De la matriz de correlación sabemos que estas columnas están altamente correlacionadas con las columnasmean radius,perimeter,area.
2.6.2. Factor de Inflación de la Varianza (VIF)#
Para abordar la multicolinealidad, se pueden aplicar técnicas como la regularización o la selección de características para, seleccionar un subconjunto de variables independientes que no estén altamente correlacionadas entre sí. En esta sección, nos centraremos en la más común: VIF (Factores de Inflación de la Varianza).
El
VIFdetermina la fuerza de la correlación entre las variables independientes. Se pronostica tomando una variable y comparándola con todas las demás. La puntuaciónVIFde una variable independiente representa hasta qué punto la variable se explica por otras variables independientes.El valor \(R^2\) se determina para averiguar hasta qué punto una variable independiente es descrita por las demás variables independientes. Un valor alto de \(R^{2}\) significa que la variable está muy correlacionada con las demás variables. Esto se refleja en el
VIF, que se indica a continuación:
Así, cuanto más se acerque el valor de \(R^2\) a 1, mayor será el valor de
VIFy mayor la multicolinealidad con la variable independiente concreta.
Observación
Un valor VIF de 1: Sin multicolinealidad (variable perfectamente independiente).
Un valor VIF entre 1 y 5: Multicolinealidad baja a moderada (no se considera problemática).
Un valor VIF entre 5 y 10: Multicolinealidad moderada a alta (considerada problemática).
Un valor VIF superior a 10: Multicolinealidad alta (preocupación grave, requiere medidas).
from statsmodels.stats.outliers_influence import variance_inflation_factor
def VIF_calculation(X):
VIF = pd.DataFrame()
VIF["variable"] = X.columns
VIF["VIF"] = [variance_inflation_factor(X.values, i) for i in range(X.shape[1])]
VIF = VIF.sort_values('VIF', ascending=False).reset_index(drop = True)
return(VIF)
def delete_multicollinearity(df, target_name, VIF_threshold):
X = df.drop(target_name, axis=1)
VIF_mat = VIF_calculation(X)
n_VIF = VIF_mat["VIF"][0]
if (n_VIF <= VIF_threshold):
print("There is no multicollinearity!")
else:
while (n_VIF > VIF_threshold):
X = X.drop(VIF_mat["variable"][0], axis=1)
VIF_mat = VIF_calculation(X)
n_VIF = VIF_mat["VIF"][0]
display(VIF_mat)
return X
df_copy = delete_multicollinearity(df_copy, "diagnosis", 10)
| variable | VIF | |
|---|---|---|
| 0 | symmetry error | 8.648328 |
| 1 | smoothness error | 8.347757 |
| 2 | fractal dimension error | 7.644681 |
| 3 | texture error | 7.103564 |
| 4 | concavity error | 6.666504 |
| 5 | worst concavity | 4.620458 |
| 6 | area error | 2.190762 |
df_copy.head()
| texture error | area error | smoothness error | concavity error | symmetry error | fractal dimension error | worst concavity | |
|---|---|---|---|---|---|---|---|
| 0 | 0.9053 | 153.40 | 0.006399 | 0.05373 | 0.03003 | 0.006193 | 0.7119 |
| 1 | 0.7339 | 74.08 | 0.005225 | 0.01860 | 0.01389 | 0.003532 | 0.2416 |
| 2 | 0.7869 | 94.03 | 0.006150 | 0.03832 | 0.02250 | 0.004571 | 0.4504 |
| 3 | 1.1560 | 27.23 | 0.009110 | 0.05661 | 0.05963 | 0.009208 | 0.6869 |
| 4 | 0.7813 | 94.44 | 0.011490 | 0.05688 | 0.01756 | 0.005115 | 0.4000 |
corr = df_copy.corr().round(2)
cmap = sns.diverging_palette(220, 10, as_cmap=True)
mask = np.zeros_like(corr)
mask[np.triu_indices_from(mask)] = True
sns.set(font_scale=1.8)
f, ax = plt.subplots(figsize=(20, 20))
sns.heatmap(corr, mask=mask, cmap=cmap, vmin=-1, vmax=1, center=0, square=True, linewidths=.5,
cbar_kws={"shrink": .5}, annot=True)
plt.tight_layout()
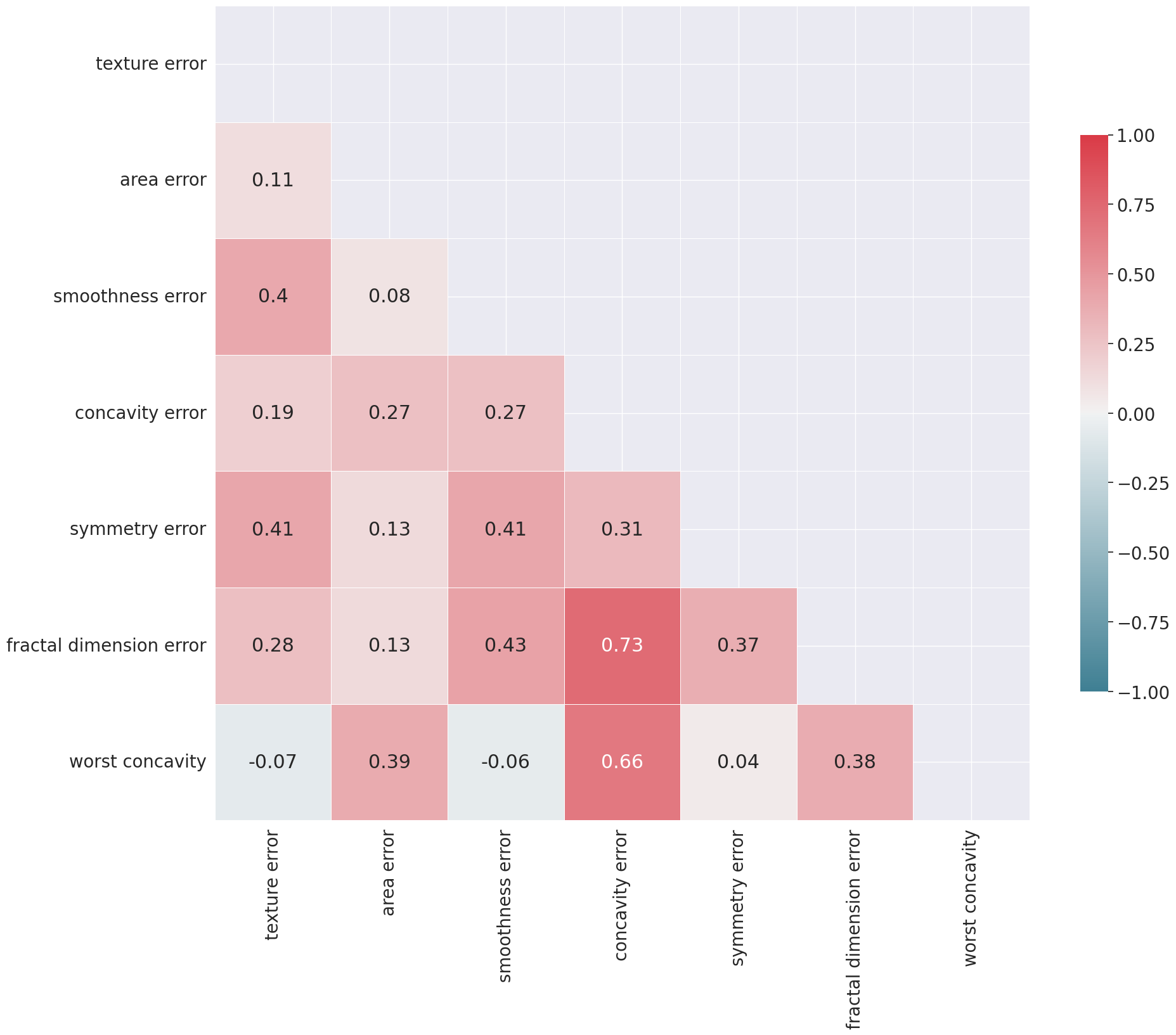
¿Debo siempre eliminar variables que presentan multicolinealidad?
La multicolinealidad afecta modelos lineales e interpretativos, pero no es un problema en modelos más complejos
Debe eliminarse (afecta estabilidad e interpretación):
Regresión Lineal y Logística → Inestabilidad en coeficientes, detectada con VIF.
Linear Discriminant Analysis (LDA) → Depende de matrices de covarianza, afectadas por multicolinealidad.
Ridge y Lasso → Ridge la mitiga, Lasso selecciona algunas variables.
No es un problema grave (modelos robustos):
Árboles de Decisión (Random Forest, XGBoost) → Seleccionan variables jerárquicamente.
SVM (kernels no lineales) → Puede aumentar costo computacional, pero no afecta resultados.
Redes Neuronales → No dependen de relaciones lineales, pero pueden sobreajustar con muchas variables redundantes.
KNN → No usa coeficientes, multicolinealidad irrelevante.
2.7. Selección del modelo K-NN#
División en entrenamiento (train) y prueba (test). Dividimos la variable objetivo y las variables independientes. A continuación, evaluamos el rendimiento del conjunto de entrenamiento y de prueba con diferentes números de vecinos
Utilizaremos en el presente problema las columnas obtenidas luego de aplicar el Factor de Inflación de la Varianza (VIF). Pude verificar que sucede cuando utiliza el dataset inicial, en el cual se retiraron de manera manual varias características, con base en la matriz de correlación
X = df_copy
y = df['diagnosis']
import numpy as np
import pandas as pd
import matplotlib
import matplotlib.pyplot as plt
from sklearn.datasets import load_breast_cancer
from sklearn.model_selection import train_test_split, cross_val_score, GridSearchCV, learning_curve
from sklearn.neighbors import KNeighborsClassifier
from sklearn.preprocessing import StandardScaler
from sklearn.pipeline import Pipeline
from sklearn.metrics import (classification_report, ConfusionMatrixDisplay,
RocCurveDisplay, roc_auc_score)
X_train, X_test, y_train, y_test = train_test_split(
X, y, stratify=y, test_size=0.2, random_state=66
)
neighbors_settings = range(1, 21)
# Metodo A: Loop manual + cross_val_score
cv_auc_manual = []
for n_neighbors in neighbors_settings:
pipe = Pipeline([
("scaler", StandardScaler()),
("knn", KNeighborsClassifier(n_neighbors=n_neighbors))
])
cv_scores = cross_val_score(pipe, X_train, y_train, cv=5, scoring="roc_auc")
cv_auc_manual.append(cv_scores.mean())
best_k_manual = list(neighbors_settings)[np.argmax(cv_auc_manual)]
# Metodo B: GridSearchCV
pipe_grid = Pipeline([
("scaler", StandardScaler()),
("knn", KNeighborsClassifier())
])
grid_search = GridSearchCV(
pipe_grid,
{"knn__n_neighbors": list(neighbors_settings)},
cv=5, scoring="roc_auc", return_train_score=True
)
grid_search.fit(X_train, y_train)
best_k_grid = grid_search.best_params_["knn__n_neighbors"]
cv_auc_grid = grid_search.cv_results_["mean_test_score"]
cv_train_auc = grid_search.cv_results_["mean_train_score"]
gap = cv_train_auc - cv_auc_grid
# Comparacion numerica
print(f"Mejor k - Loop manual : {best_k_manual} (CV AUC: {max(cv_auc_manual):.6f})")
print(f"Mejor k - GridSearchCV: {best_k_grid} (CV AUC: {grid_search.best_score_:.6f})")
print(f"Scores identicos: {np.allclose(cv_auc_manual, cv_auc_grid, atol=1e-10)}\n")
# Predicciones del modelo optimo
y_pred = grid_search.predict(X_test)
y_proba = grid_search.predict_proba(X_test)[:, 1]
# Learning curve
train_sizes, lc_train, lc_val = learning_curve(
grid_search.best_estimator_,
X_train, y_train,
cv=5, scoring="roc_auc",
train_sizes=np.linspace(0.1, 1.0, 10),
shuffle=True, random_state=66
)
lc_train_mean = lc_train.mean(axis=1)
lc_train_std = lc_train.std(axis=1)
lc_val_mean = lc_val.mean(axis=1)
lc_val_std = lc_val.std(axis=1)
ks = list(neighbors_settings)
matplotlib.rc_file_defaults()
# Figura 1: Equivalencia Loop vs GridSearchCV
fig, axes = plt.subplots(1, 2, figsize=(14, 5), sharey=True)
ax = axes[0]
ax.plot(ks, cv_auc_manual, marker="^", linestyle="--", color="green",
label="CV-5 AUC (loop manual)")
ax.axvline(best_k_manual, color="gray", linestyle=":")
ax.set_title(f"Metodo A - Loop + cross_val_score\nMejor k={best_k_manual}")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("CV ROC-AUC")
ax.legend(fontsize=9)
ax = axes[1]
ax.plot(ks, cv_auc_grid, marker="^", linestyle="--", color="purple",
label="CV-5 AUC (GridSearchCV)")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title(f"Metodo B - GridSearchCV\nMejor k={best_k_grid}")
ax.set_xlabel("n_neighbors")
ax.legend(fontsize=9)
plt.suptitle("Equivalencia demostrada: Loop manual = GridSearchCV (roc_auc)",
fontsize=13, fontweight="bold")
plt.tight_layout()
plt.show()
# Figura 2: Curva ROC + Matriz de confusion
fig, axes = plt.subplots(1, 2, figsize=(13, 5))
RocCurveDisplay.from_estimator(
grid_search.best_estimator_, X_test, y_test,
ax=axes[0], color="darkorange", name=f"KNN k={best_k_grid}"
)
axes[0].plot([0, 1], [0, 1], "k--", label="Clasificador aleatorio")
axes[0].set_title(f"Curva ROC (k={best_k_grid})")
axes[0].legend()
ConfusionMatrixDisplay.from_estimator(
grid_search.best_estimator_, X_test, y_test,
display_labels=cancer.target_names, cmap="Blues", ax=axes[1]
)
axes[1].set_title(f"Matriz de confusion (k={best_k_grid})")
plt.suptitle("Evaluacion del modelo optimo", fontsize=13, fontweight="bold")
plt.tight_layout()
plt.show()
# Figura 3: Diagnostico de sobreajuste
fig, axes = plt.subplots(1, 3, figsize=(18, 5))
ax = axes[0]
ax.plot(ks, cv_train_auc, label="Train AUC", marker="o", color="steelblue")
ax.plot(ks, cv_auc_grid, label="Val AUC", marker="s", color="darkorange")
ax.fill_between(ks, cv_auc_grid, cv_train_auc, alpha=0.15, color="red",
label="Brecha")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title("Train AUC vs Val AUC por k")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("ROC-AUC")
ax.legend(fontsize=8)
ax = axes[1]
ax.bar(ks, gap,
color=["red" if g > 0.02 else "steelblue" for g in gap],
alpha=0.8, edgecolor="white")
ax.axhline(0.02, color="red", linestyle="--", linewidth=1.2, label="Umbral 0.02")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title("Brecha Train - Val AUC")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("Delta AUC")
ax.legend(fontsize=8)
ax = axes[2]
ax.plot(train_sizes, lc_train_mean, "o-", color="steelblue", label="Train AUC")
ax.plot(train_sizes, lc_val_mean, "s-", color="darkorange", label="Val AUC (CV-5)")
ax.fill_between(train_sizes,
lc_train_mean - lc_train_std,
lc_train_mean + lc_train_std, alpha=0.12, color="steelblue")
ax.fill_between(train_sizes,
lc_val_mean - lc_val_std,
lc_val_mean + lc_val_std, alpha=0.12, color="darkorange")
ax.set_title(f"Learning curve (k={best_k_grid})")
ax.set_xlabel("Tamano del conjunto de entrenamiento")
ax.set_ylabel("ROC-AUC")
ax.legend(fontsize=8)
plt.suptitle("Diagnostico de sobreajuste", fontsize=13, fontweight="bold")
plt.tight_layout()
plt.show()
# Veredicto
gap_best = cv_train_auc[best_k_grid - 1] - cv_auc_grid[best_k_grid - 1]
converge = abs(lc_train_mean[-1] - lc_val_mean[-1]) < 0.02
print(f"k optimo : {best_k_grid}")
print(f"CV Train AUC : {cv_train_auc[best_k_grid-1]:.4f}")
print(f"CV Val AUC : {cv_auc_grid[best_k_grid-1]:.4f}")
print(f"Brecha train-val: {gap_best:.4f} ({'OK' if gap_best < 0.02 else 'Posible sobreajuste'})")
print(f"Learning curve : {'Converge' if converge else 'No converge'}")
print(f"Test AUC final : {roc_auc_score(y_test, y_proba):.4f}\n")
print(classification_report(y_test, y_pred, target_names=cancer.target_names))
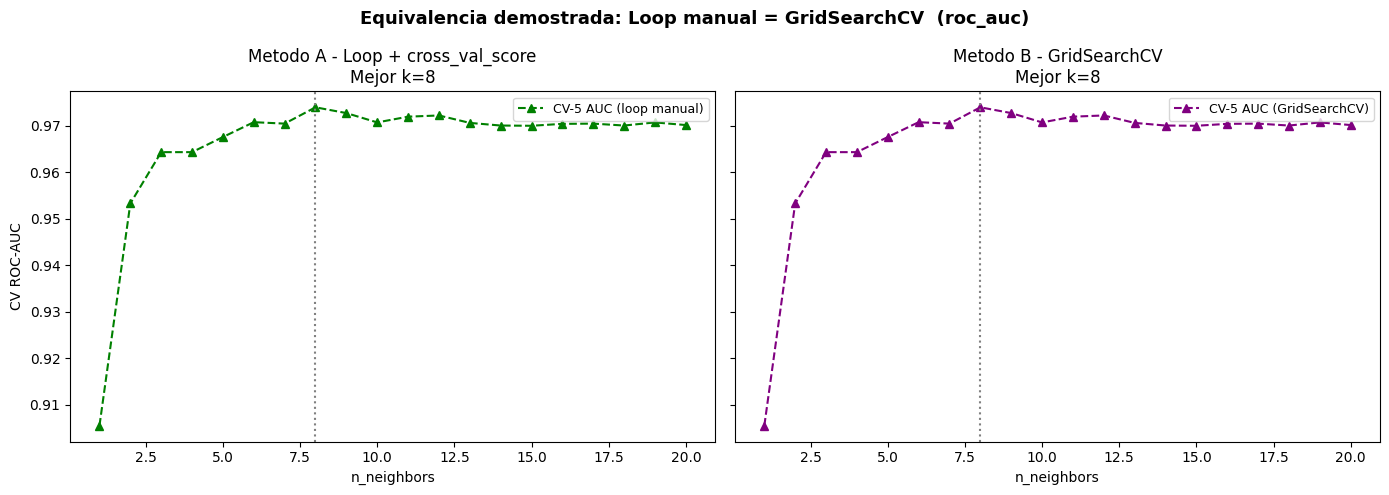
Mejor k - Loop manual : 8 (CV AUC: 0.973994)
Mejor k - GridSearchCV: 8 (CV AUC: 0.973994)
Scores identicos: True
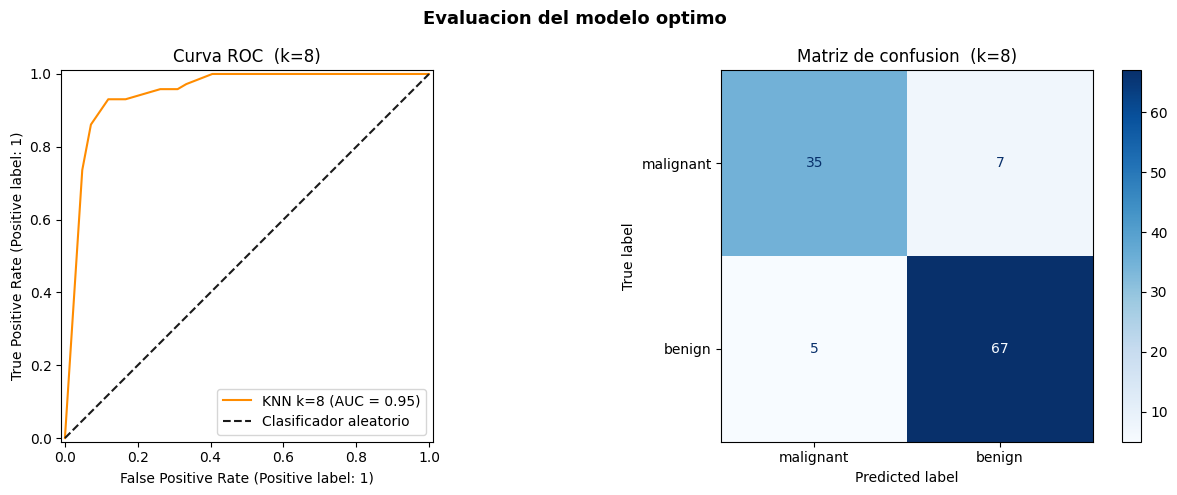
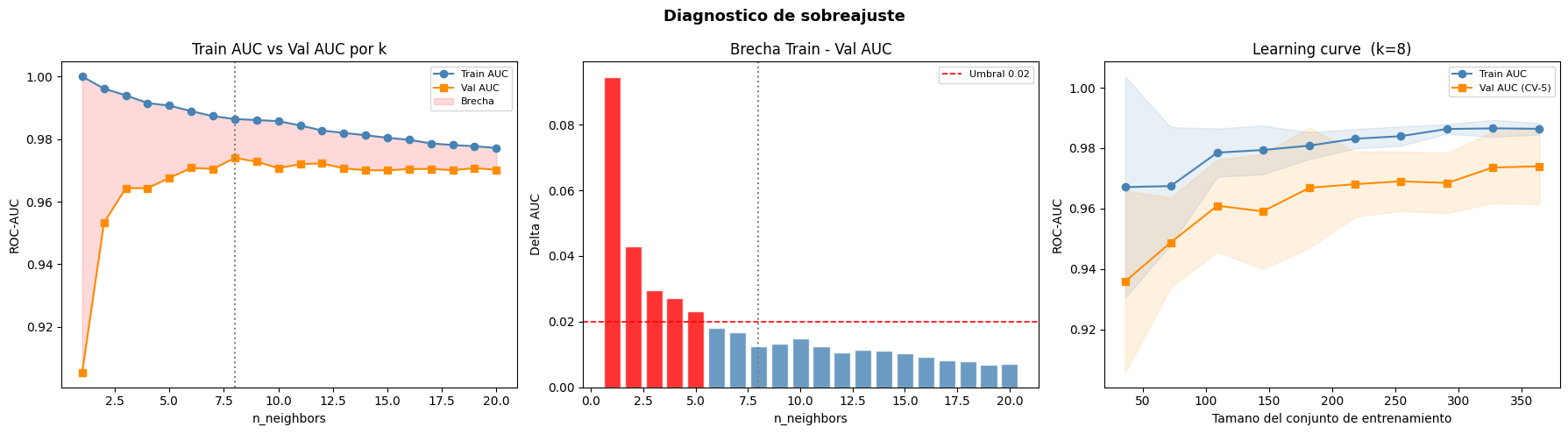
k optimo : 8
CV Train AUC : 0.9864
CV Val AUC : 0.9740
Brecha train-val: 0.0124 (OK)
Learning curve : Converge
Test AUC final : 0.9478
precision recall f1-score support
malignant 0.88 0.83 0.85 42
benign 0.91 0.93 0.92 72
accuracy 0.89 114
macro avg 0.89 0.88 0.89 114
weighted avg 0.89 0.89 0.89 114
2.8. Regresión por \(k\)-vecinos#
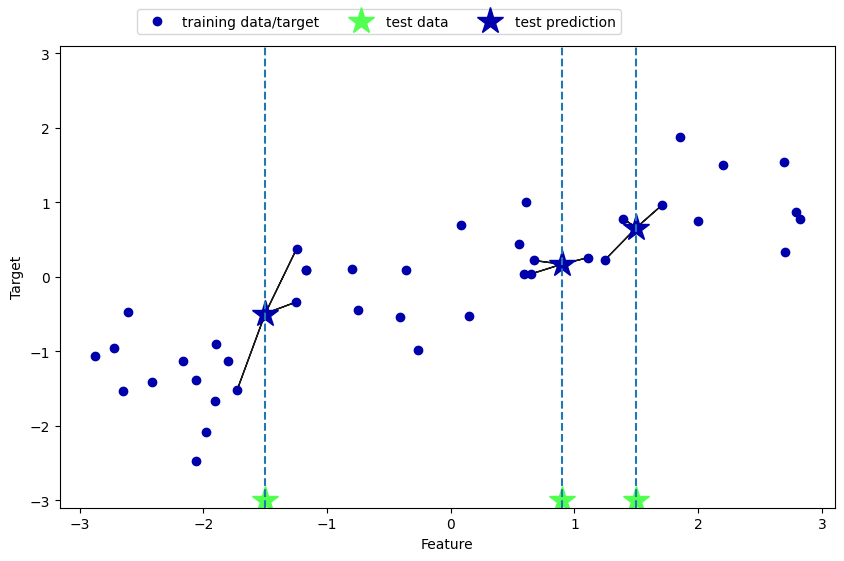
También existe una variante de regresión del algoritmo \(k\)-vecinos más cercanos. Una vez más, vamos a empezar utilizando el vecino más cercano simple, esta vez utilizando el conjunto de datos
wave. Hemos añadido tres puntos de datos de prueba como estrellas verdes en el eje \(x\). La predicción utilizando un solo vecino es sólo el valor objetivo del vecino más cercano
mglearn.plots.plot_knn_regression(n_neighbors=1)
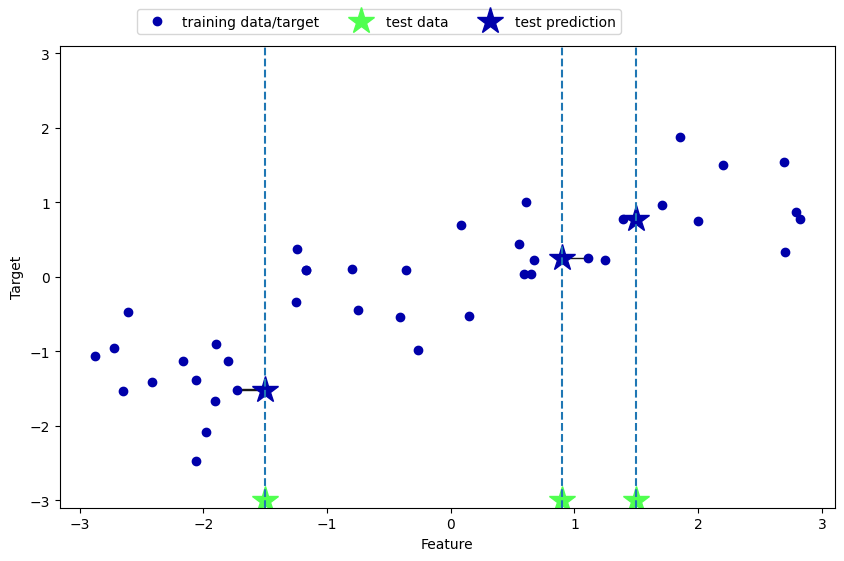
De nuevo, podemos utilizar más que el único vecino más cercano para la regresión. Cuando se utilizan varios vecinos más cercanos, la predicción es el promedio, o la media, de los vecinos
mglearn.plots.plot_knn_regression(n_neighbors=3)
El algoritmo de \(k\)-vecinos más cercanos para la regresión se implementa en la clase
KNeighbors Regressorenscikit-learn. Se utiliza de forma similar aKNeighborsClassifier
from sklearn.neighbors import KNeighborsRegressor
X, y = mglearn.datasets.make_wave(n_samples=40)
X_train, X_test, y_train, y_test = train_test_split(X, y, random_state=0)
reg = KNeighborsRegressor(n_neighbors=3)
reg.fit(X_train, y_train)
KNeighborsRegressor(n_neighbors=3)In a Jupyter environment, please rerun this cell to show the HTML representation or trust the notebook.
On GitHub, the HTML representation is unable to render, please try loading this page with nbviewer.org.
Parameters
| n_neighbors | 3 | |
| weights | 'uniform' | |
| algorithm | 'auto' | |
| leaf_size | 30 | |
| p | 2 | |
| metric | 'minkowski' | |
| metric_params | None | |
| n_jobs | None |
Ahora podemos hacer predicciones sobre el conjunto de prueba
print("Test set predictions:\n{}".format(reg.predict(X_test)))
Test set predictions:
[-0.05396539 0.35686046 1.13671923 -1.89415682 -1.13881398 -1.63113382
0.35686046 0.91241374 -0.44680446 -1.13881398]
También podemos evaluar el modelo utilizando el método score, que para los regresores devuelve la puntuación \(R^2\). La puntuación \(R^2\), también conocida como coeficiente de determinación, es una medida de predicción de un modelo de regresión, y arroja una puntuación entre 0 y 1. Un valor de 1 corresponde a una predicción perfecta, y un valor de 0 corresponde a un modelo constante que sólo predice la media de las respuestas del conjunto de entrenamiento,
y_train. Aquí, elscorees de 0.83, lo que indica un ajuste del modelo relativamente bueno.
print("Test set R^2: {:.2f}".format(reg.score(X_test, y_test)))
Test set R^2: 0.83
2.9. Análisis de KNeighborsRegressor#
Para nuestro conjunto de datos unidimensional, podemos ver cómo son las predicciones para todos los valores posibles de las características. Para ello, creamos un conjunto de datos de prueba compuesto por muchos puntos de la línea
import numpy as np
fig, axes = plt.subplots(1, 3, figsize=(15, 4))
line = np.linspace(-3, 3, 1000).reshape(-1, 1)
for n_neighbors, ax in zip([1, 3, 9], axes):
reg = KNeighborsRegressor(n_neighbors=n_neighbors)
reg.fit(X_train, y_train)
ax.plot(line, reg.predict(line))
ax.plot(X_train, y_train, '^', c=mglearn.cm2(0), markersize=8)
ax.plot(X_test, y_test, 'v', c=mglearn.cm2(1), markersize=8)
ax.set_title("{} neighbor(s)\n train score: {:.2f} test score: {:.2f}".format(n_neighbors,
reg.score(X_train, y_train),
reg.score(X_test, y_test)))
ax.set_xlabel("Feature")
ax.set_ylabel("Target")
axes[0].legend(["Model predictions", "Training data/target", "Test data/target"], loc="best");
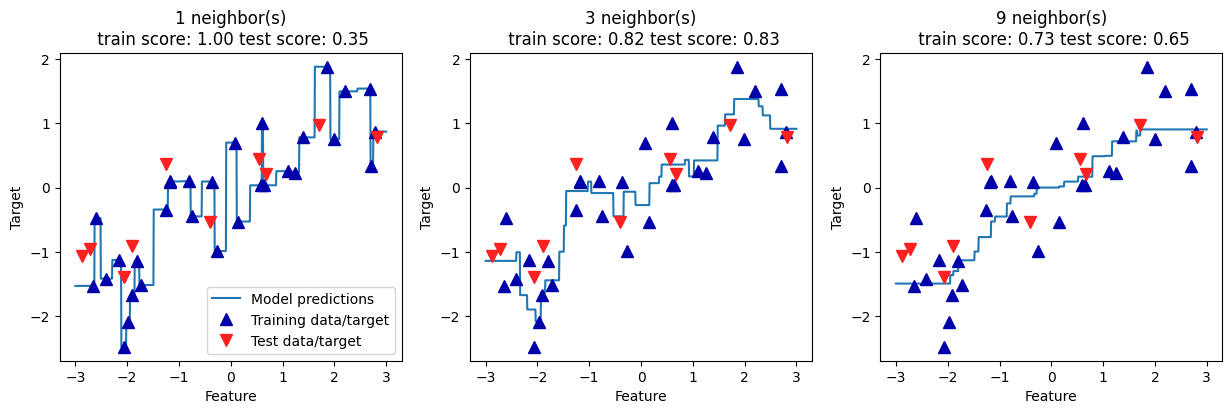
Como podemos ver en el gráfico, al utilizar un solo vecino, cada punto del conjunto de entrenamiento tiene una influencia obvia en las predicciones, y los valores predichos pasan por todos los puntos de datos. Esto conduce a una predicción muy inestable. Tener en cuenta más vecinos conduce a predicciones más suaves, pero éstas no se ajustan tan bien a los datos de entrenamiento.
2.9.1. Aplicación: World Hydropower Generation#
World Hydropower Generation: Esta sección se centra en el uso del modelo \(k\)-NN y sus hiperparamétros, para garantizar una mejor comprensión de este algoritmo. No se utilizan otros recursos como la ingeniería de características, la reducción de dimensionalidad. El conjunto de datos utilizado es una recopilación de la generación de energía de varios países europeos, medida en THh entre 2000 y 2019. Su contenido fue extraído de World in Data.
En primer lugar, se importan las librerías básicas:
pandas, matplotlibynumpyparaDataframes, Gráficosy operaciones numéricas;MinMaxScalerpara normalizar nuestros datos entre 0 y 1,train_test_splitpara ayudar a dividir el conjunto de datos (normalmente 70% entrenamiento/ 30% prueba) yneighborspara generar nuestros modelos usando kNN
import pandas as pd
import matplotlib.pyplot as plt
import numpy as np
from sklearn.preprocessing import MinMaxScaler
from sklearn.model_selection import train_test_split
from sklearn.model_selection import GridSearchCV
from sklearn import neighbors
from sklearn.metrics import mean_absolute_error
from sklearn.metrics import mean_squared_error
from sklearn.metrics import mean_squared_log_error
from sklearn.metrics import r2_score
from sklearn.metrics import explained_variance_score
Para medir la eficacia de nuestros modelos generados, utilizamoslas siguientes métricas:
mean_absolute_error (MAE): medida de los errores entre observaciones emparejadas que expresan el mismo fenómeno; \(\text{MAE}=\frac{1}{n}\sum_{j=1}^{n}|y_{j}-\hat{y}_{j}|\)
mean_squared_error (root - RMSE): la desviación estándar de los residuos (errores de predicción); \(\text{RMSE}=\sqrt{\frac{1}{n}\sum_{j=1}^{n}(y_{j}-\hat{y}_{j})^{2}}\)
mean_squared_log_error (root - RMSLE): mide la relación entre lo real y lo predicho; \(\text{RMSLE}=\sqrt{\frac{1}{n}\sum_{j=1}^{n}(\log(y_{j}+1)-\log(\hat{y}_{j}+1))^{2}}\)
r2_score (R2):: coeficiente de determinación, la proporción de la varianza en la variable dependiente que es predecible a partir de la(s) variable(s) independiente(s); \(R^{2}=1-\sum_{j=1}^{n}(y_{j}-\hat{y}_{j})^{2}/\sum_{j=1}^{n}(y_{j}-\overline{y}_{j})^{2}\)
explained_variance_score (EVS): mide la discrepancia entre un modelo y los datos reales \(\text{EVS}=1-\text{Var}(y-\hat{y})/\text{Var}(y).\)
Preprocesamiento de datos: Inicialmente, los datos son importados, y se excluyen las columnas categóricas (en este caso, sólo"Country"). Para transformar el conjunto de datos y mantenerlo como unDataframe, se utiliza la libreríascalerdentro de la librería Dataframe, normalizando los datos entre 0 y 1, y manteniendo las propiedades del dataframe. Después de esto, se llama a la funcióndescribe, para mostrar algunos datos importantes sobre eldataframe, comomean, max, min, stdy otros.
pd.options.display.float_format = '{:.4f}'.format
scaler = MinMaxScaler(feature_range=(0, 1))
df_power = pd.read_csv('https://raw.githubusercontent.com/lihkir/Data/main/Hydropower_Consumption.csv', sep=',')
df_power.info()
<class 'pandas.core.frame.DataFrame'>
RangeIndex: 153 entries, 0 to 152
Data columns (total 21 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 Country 153 non-null object
1 2000 153 non-null int64
2 2001 153 non-null int64
3 2002 153 non-null int64
4 2003 153 non-null int64
5 2004 153 non-null int64
6 2005 153 non-null int64
7 2006 153 non-null int64
8 2007 153 non-null int64
9 2008 153 non-null int64
10 2009 153 non-null int64
11 2010 153 non-null int64
12 2011 153 non-null int64
13 2012 153 non-null int64
14 2013 153 non-null int64
15 2014 153 non-null int64
16 2015 153 non-null int64
17 2016 153 non-null int64
18 2017 153 non-null int64
19 2018 153 non-null int64
20 2019 153 non-null int64
dtypes: int64(20), object(1)
memory usage: 25.2+ KB
df_power.head()
| Country | 2000 | 2001 | 2002 | 2003 | 2004 | 2005 | 2006 | 2007 | 2008 | ... | 2010 | 2011 | 2012 | 2013 | 2014 | 2015 | 2016 | 2017 | 2018 | 2019 | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | Afghanistan | 312 | 498 | 555 | 63 | 565 | 59 | 637 | 748 | 542 | ... | 751 | 595 | 71 | 804 | 895 | 989 | 1025 | 105 | 105 | 107 |
| 1 | Africa | 75246 | 80864 | 85181 | 82873 | 87405 | 89066 | 92241 | 95341 | 97157 | ... | 107427 | 110445 | 110952 | 117673 | 123727 | 115801 | 123816 | 130388 | 132735 | 0 |
| 2 | Albania | 4548 | 3519 | 3477 | 5117 | 5411 | 5319 | 4951 | 276 | 3759 | ... | 7673 | 4036 | 4725 | 6959 | 4726 | 5866 | 7136 | 448 | 448 | 4018 |
| 3 | Algeria | 54 | 69 | 57 | 265 | 251 | 555 | 218 | 226 | 283 | ... | 173 | 378 | 389 | 99 | 193 | 145 | 72 | 56 | 117 | 152 |
| 4 | Angola | 903 | 1007 | 1132 | 1229 | 1733 | 2197 | 2638 | 2472 | 3103 | ... | 3666 | 3967 | 3734 | 4719 | 4991 | 5037 | 5757 | 7576 | 7576 | 8422 |
5 rows × 21 columns
countries = df_power.Country
df_power = df_power.drop(columns = ["Country"])
df_power = pd.DataFrame(scaler.fit_transform(df_power),
columns=['2000','2001','2002','2003','2004','2005',
'2006','2007','2008','2009','2010','2011',
'2012','2013','2014','2015','2016','2017',
'2018','2019'])
df_power.describe()
| 2000 | 2001 | 2002 | 2003 | 2004 | 2005 | 2006 | 2007 | 2008 | 2009 | 2010 | 2011 | 2012 | 2013 | 2014 | 2015 | 2016 | 2017 | 2018 | 2019 | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| count | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 | 153.0000 |
| mean | 0.0327 | 0.0353 | 0.0355 | 0.0328 | 0.0419 | 0.0390 | 0.0415 | 0.0434 | 0.0371 | 0.0445 | 0.0328 | 0.0433 | 0.0352 | 0.0290 | 0.0282 | 0.0265 | 0.0306 | 0.0296 | 0.0388 | 0.0259 |
| std | 0.1229 | 0.1262 | 0.1278 | 0.1249 | 0.1372 | 0.1364 | 0.1366 | 0.1440 | 0.1293 | 0.1493 | 0.1208 | 0.1459 | 0.1294 | 0.1121 | 0.1062 | 0.1031 | 0.1117 | 0.1110 | 0.1317 | 0.1043 |
| min | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 | 0.0000 |
| 25% | 0.0002 | 0.0003 | 0.0003 | 0.0003 | 0.0003 | 0.0004 | 0.0003 | 0.0004 | 0.0004 | 0.0003 | 0.0004 | 0.0002 | 0.0004 | 0.0002 | 0.0003 | 0.0002 | 0.0002 | 0.0002 | 0.0003 | 0.0002 |
| 50% | 0.0027 | 0.0030 | 0.0026 | 0.0027 | 0.0037 | 0.0028 | 0.0031 | 0.0039 | 0.0032 | 0.0035 | 0.0043 | 0.0040 | 0.0034 | 0.0025 | 0.0024 | 0.0019 | 0.0025 | 0.0020 | 0.0029 | 0.0019 |
| 75% | 0.0116 | 0.0128 | 0.0119 | 0.0118 | 0.0155 | 0.0107 | 0.0149 | 0.0151 | 0.0147 | 0.0152 | 0.0145 | 0.0156 | 0.0140 | 0.0096 | 0.0121 | 0.0086 | 0.0117 | 0.0113 | 0.0171 | 0.0097 |
| max | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 | 1.0000 |
Ahora, el objetivo es crear un modelo que prediga la generación de energía para 2019, basándose en los 18 años anteriores (2000 - 2018) con al menos un 75% de precisión. Para ello, el conjunto de datos se separó en
Xey, siendoXdatos de predicción eylo que se pretende predecir. Para ello, se dividen en entrenamiento (70%) y prueba (30%).
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
from sklearn.preprocessing import MinMaxScaler
from sklearn.model_selection import train_test_split, GridSearchCV, cross_validate
from sklearn.neighbors import KNeighborsRegressor
from sklearn.pipeline import Pipeline
from sklearn.metrics import (mean_absolute_error, mean_squared_error,
mean_squared_log_error, r2_score,
explained_variance_score)
from scipy import stats
pd.options.display.float_format = '{:.4f}'.format
# Datos
df_power = pd.read_csv(
'https://raw.githubusercontent.com/lihkir/Data/main/Hydropower_Consumption.csv',
sep=','
)
countries = df_power["Country"]
df_power = df_power.drop(columns=["Country"])
# X e y sobre datos SIN escalar
# El escalado va dentro del Pipeline para evitar data-leakage
X = df_power.drop(columns=["2019"])
y = df_power["2019"]
# Split ANTES de cualquier transformacion
X_train, X_test, y_train, y_test = train_test_split(
X, y, test_size=0.3, random_state=0
)
neighbors_settings = range(1, 21)
# Metodo A: Loop manual + cross_validate
# Pipeline garantiza que MinMaxScaler ajuste solo sobre train en cada fold
cv_val_scores = []
cv_train_scores = []
fold_gaps_por_k = []
for n_neighbors in neighbors_settings:
pipe = Pipeline([
("scaler", MinMaxScaler(feature_range=(0, 1))),
("knn", KNeighborsRegressor(n_neighbors=n_neighbors))
])
cv_results = cross_validate(
pipe, X_train, y_train,
cv=5,
scoring="r2",
return_train_score=True
)
fold_train = cv_results["train_score"]
fold_val = cv_results["test_score"]
cv_train_scores.append(fold_train.mean())
cv_val_scores.append(fold_val.mean())
fold_gaps_por_k.append(fold_train - fold_val)
best_k_manual = list(neighbors_settings)[np.argmax(cv_val_scores)]
# Metodo B: GridSearchCV
pipe_grid = Pipeline([
("scaler", MinMaxScaler(feature_range=(0, 1))),
("knn", KNeighborsRegressor())
])
grid_search = GridSearchCV(
pipe_grid,
{"knn__n_neighbors": list(neighbors_settings)},
cv=5,
scoring="r2",
return_train_score=True
)
grid_search.fit(X_train, y_train)
best_k_grid = grid_search.best_params_["knn__n_neighbors"]
cv_r2_grid = grid_search.cv_results_["mean_test_score"]
cv_train_r2 = grid_search.cv_results_["mean_train_score"]
gap = cv_train_r2 - cv_r2_grid
# Comparacion Loop vs GridSearchCV
print("Mejor k - Loop manual : {} (CV R2: {:.6f})".format(best_k_manual, max(cv_val_scores)))
print("Mejor k - GridSearchCV: {} (CV R2: {:.6f})".format(best_k_grid, grid_search.best_score_))
print("Scores identicos :", np.allclose(cv_val_scores, cv_r2_grid, atol=1e-10))
print()
# Predicciones del modelo optimo
y_pred = grid_search.predict(X_test)
# Metricas sobre test
# RMSLE requiere valores positivos: MinMaxScaler garantiza y >= 0
r2_val = r2_score(y_test, y_pred)
evs_val = explained_variance_score(y_test, y_pred)
mae_val = mean_absolute_error(y_test, y_pred)
rmse_val = np.sqrt(mean_squared_error(y_test, y_pred))
rmsle_val = np.sqrt(mean_squared_log_error(y_test, np.clip(y_pred, 0, None)))
print("Metricas en test (k={})".format(best_k_grid))
print(" R2 : {:.4f}".format(r2_val))
print(" EVS : {:.4f}".format(evs_val))
print(" MAE : {:.4f}".format(mae_val))
print(" RMSE : {:.4f}".format(rmse_val))
print(" RMSLE: {:.4f}".format(rmsle_val))
print()
# Diagnostico de sobreajuste: t-test pareado por k
print("T-test pareado por k (H0: brecha = 0):")
for i, k in enumerate(neighbors_settings):
t_stat, p_valor = stats.ttest_1samp(fold_gaps_por_k[i], popmean=0)
sig = "significativa" if p_valor < 0.05 else "no significativa"
print(" k={:2d} brecha={:.4f} p={:.4f} -> {}".format(
k, gap[i], p_valor, sig))
print()
# T-test pareado: brecha k=1 vs brecha k optimo
gap_k1 = fold_gaps_por_k[0]
gap_best = fold_gaps_por_k[best_k_grid - 1]
t2, p2 = stats.ttest_rel(gap_k1, gap_best)
print("T-test pareado: brecha k=1 vs brecha k={}".format(best_k_grid))
print(" Brecha media k=1 : {:.4f}".format(gap_k1.mean()))
print(" Brecha media k optimo : {:.4f}".format(gap_best.mean()))
print(" p-valor : {:.4f}".format(p2))
if p2 < 0.05:
print(" k=1 sobreajusta significativamente mas que k={}".format(best_k_grid))
else:
print(" Diferencia de brechas no significativa")
print()
# Veredicto final
gap_best_val = cv_train_r2[best_k_grid - 1] - cv_r2_grid[best_k_grid - 1]
t_final, p_final = stats.ttest_1samp(fold_gaps_por_k[best_k_grid - 1], popmean=0)
print("Veredicto k optimo ({})".format(best_k_grid))
print(" CV Train R2 : {:.4f}".format(cv_train_r2[best_k_grid - 1]))
print(" CV Val R2 : {:.4f}".format(cv_r2_grid[best_k_grid - 1]))
print(" Brecha media : {:.4f}".format(gap_best_val))
print(" p-valor : {:.4f}".format(p_final))
print(" Sobreajuste :", "detectable" if p_final < 0.05 else "no detectable")
print()
# Figura 1: Curva codo — RMSLE por k (loop manual sobre test para compatibilidad visual)
rmsle_por_k = []
for k in neighbors_settings:
pipe_tmp = Pipeline([
("scaler", MinMaxScaler()),
("knn", KNeighborsRegressor(n_neighbors=k))
])
pipe_tmp.fit(X_train, y_train)
y_tmp = pipe_tmp.predict(X_test)
rmsle_por_k.append(np.sqrt(mean_squared_log_error(y_test, np.clip(y_tmp, 0, None))))
plt.figure(figsize=(8, 5))
plt.plot(list(neighbors_settings), rmsle_por_k, marker="o", color="steelblue")
plt.axvline(best_k_grid, color="gray", linestyle=":", label="k optimo={}".format(best_k_grid))
plt.xlabel("n_neighbors")
plt.ylabel("RMSLE")
plt.title("Curva codo — RMSLE por k (pipeline sin data-leakage)")
plt.legend()
plt.tight_layout()
plt.show()
# Figura 2: CV R2 Loop vs GridSearchCV
fig, axes = plt.subplots(1, 2, figsize=(14, 5), sharey=True)
ax = axes[0]
ax.plot(list(neighbors_settings), cv_val_scores, marker="^", linestyle="--",
color="green", label="CV-5 R2 (loop manual)")
ax.axvline(best_k_manual, color="gray", linestyle=":")
ax.set_title("Metodo A - Loop + cross_validate\nMejor k={}".format(best_k_manual))
ax.set_xlabel("n_neighbors")
ax.set_ylabel("CV R2")
ax.legend(fontsize=9)
ax = axes[1]
ax.plot(list(neighbors_settings), cv_r2_grid, marker="^", linestyle="--",
color="purple", label="CV-5 R2 (GridSearchCV)")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title("Metodo B - GridSearchCV\nMejor k={}".format(best_k_grid))
ax.set_xlabel("n_neighbors")
ax.legend(fontsize=9)
plt.suptitle("Equivalencia demostrada: Loop manual = GridSearchCV (r2)",
fontsize=13, fontweight="bold")
plt.tight_layout()
plt.show()
# Figura 3: Diagnostico de sobreajuste
fig, axes = plt.subplots(1, 2, figsize=(14, 5))
ax = axes[0]
ax.plot(list(neighbors_settings), cv_train_r2, label="Train R2", marker="o", color="steelblue")
ax.plot(list(neighbors_settings), cv_r2_grid, label="Val R2", marker="s", color="darkorange")
ax.fill_between(list(neighbors_settings), cv_r2_grid, cv_train_r2,
alpha=0.15, color="red", label="Brecha")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title("Train R2 vs Val R2 por k")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("R2")
ax.legend(fontsize=8)
ax = axes[1]
ax.bar(list(neighbors_settings), gap,
color=["red" if g > 0.05 else "steelblue" for g in gap],
alpha=0.8, edgecolor="white")
ax.axhline(0.05, color="red", linestyle="--", linewidth=1.2, label="Umbral 0.05")
ax.axvline(best_k_grid, color="gray", linestyle=":")
ax.set_title("Brecha Train - Val R2")
ax.set_xlabel("n_neighbors")
ax.set_ylabel("Delta R2")
ax.legend(fontsize=8)
plt.suptitle("Diagnostico de sobreajuste", fontsize=13, fontweight="bold")
plt.tight_layout()
plt.show()
# Figura 4: Prediccion vs Test por pais
country_test = countries.iloc[y_test.index].values
data_pred = pd.DataFrame({"Test": y_test.values, "Prediction": y_pred},
index=country_test)
plt.figure(figsize=(20, 8))
plt.plot(data_pred.index, data_pred.Test, label="Test")
plt.plot(data_pred.index, data_pred.Prediction, label="Prediction")
plt.xticks(rotation=90, fontsize=10)
plt.xlabel("Country")
plt.ylabel("Hydropower Generation (normalizado)")
plt.title("Prediccion vs Test — k={} (pipeline, sin data-leakage)".format(best_k_grid))
plt.legend(loc="upper right")
plt.tight_layout()
plt.show()
Mejor k - Loop manual : 5 (CV R2: 0.483347)
Mejor k - GridSearchCV: 5 (CV R2: 0.483347)
Scores identicos : True
Metricas en test (k=5)
R2 : 0.5489
EVS : 0.5764
MAE : 30576.8304
RMSE : 95719.3322
RMSLE: 2.0041
T-test pareado por k (H0: brecha = 0):
k= 1 brecha=0.7628 p=0.0073 -> significativa
k= 2 brecha=0.3928 p=0.0191 -> significativa
k= 3 brecha=0.2017 p=0.1407 -> no significativa
k= 4 brecha=0.1273 p=0.2869 -> no significativa
k= 5 brecha=0.0371 p=0.7812 -> no significativa
k= 6 brecha=-0.0016 p=0.9914 -> no significativa
k= 7 brecha=-0.0138 p=0.9197 -> no significativa
k= 8 brecha=-0.0092 p=0.9491 -> no significativa
k= 9 brecha=-0.0380 p=0.8067 -> no significativa
k=10 brecha=-0.0474 p=0.7545 -> no significativa
k=11 brecha=-0.0524 p=0.7280 -> no significativa
k=12 brecha=-0.0488 p=0.7343 -> no significativa
k=13 brecha=-0.0539 p=0.7057 -> no significativa
k=14 brecha=-0.0536 p=0.7000 -> no significativa
k=15 brecha=-0.0553 p=0.6878 -> no significativa
k=16 brecha=-0.0818 p=0.5871 -> no significativa
k=17 brecha=-0.1559 p=0.3469 -> no significativa
k=18 brecha=-0.1723 p=0.2916 -> no significativa
k=19 brecha=-0.1644 p=0.2957 -> no significativa
k=20 brecha=-0.1593 p=0.2960 -> no significativa
T-test pareado: brecha k=1 vs brecha k=5
Brecha media k=1 : 0.7628
Brecha media k optimo : 0.0371
p-valor : 0.0145
k=1 sobreajusta significativamente mas que k=5
Veredicto k optimo (5)
CV Train R2 : 0.5205
CV Val R2 : 0.4833
Brecha media : 0.0371
p-valor : 0.7812
Sobreajuste : no detectable
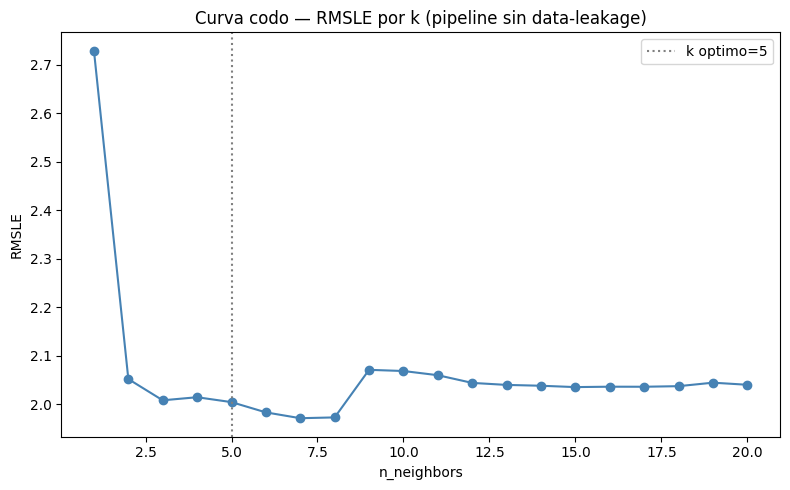
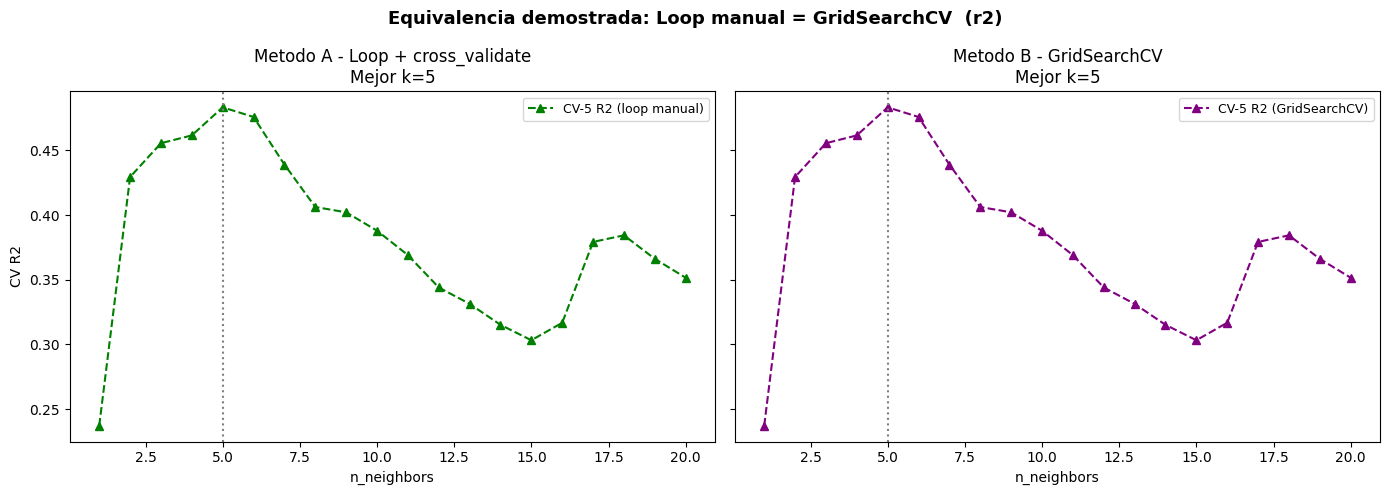
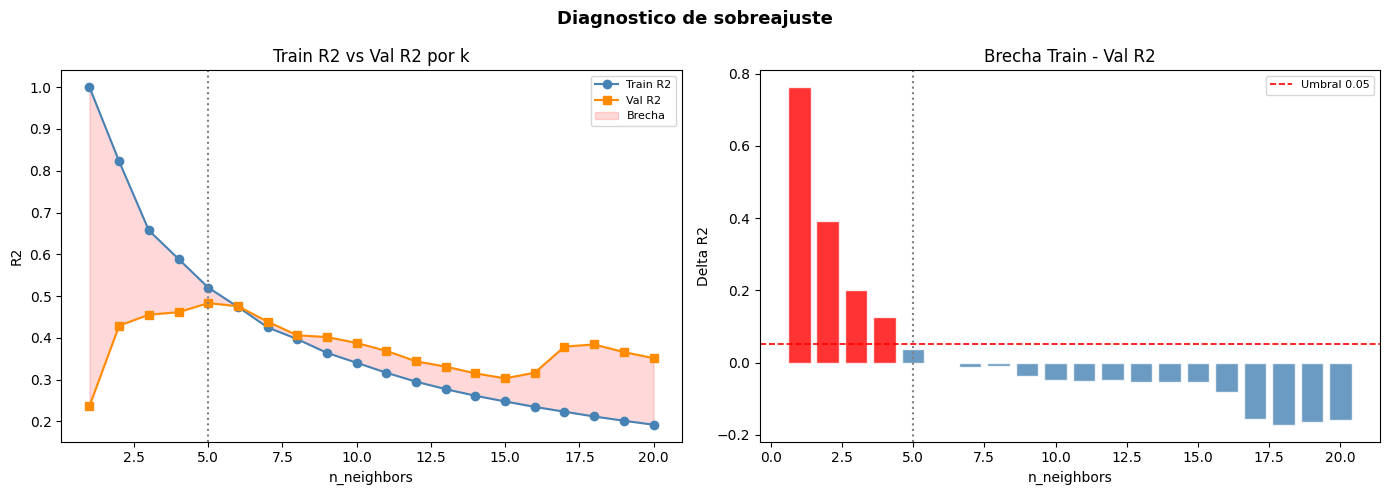
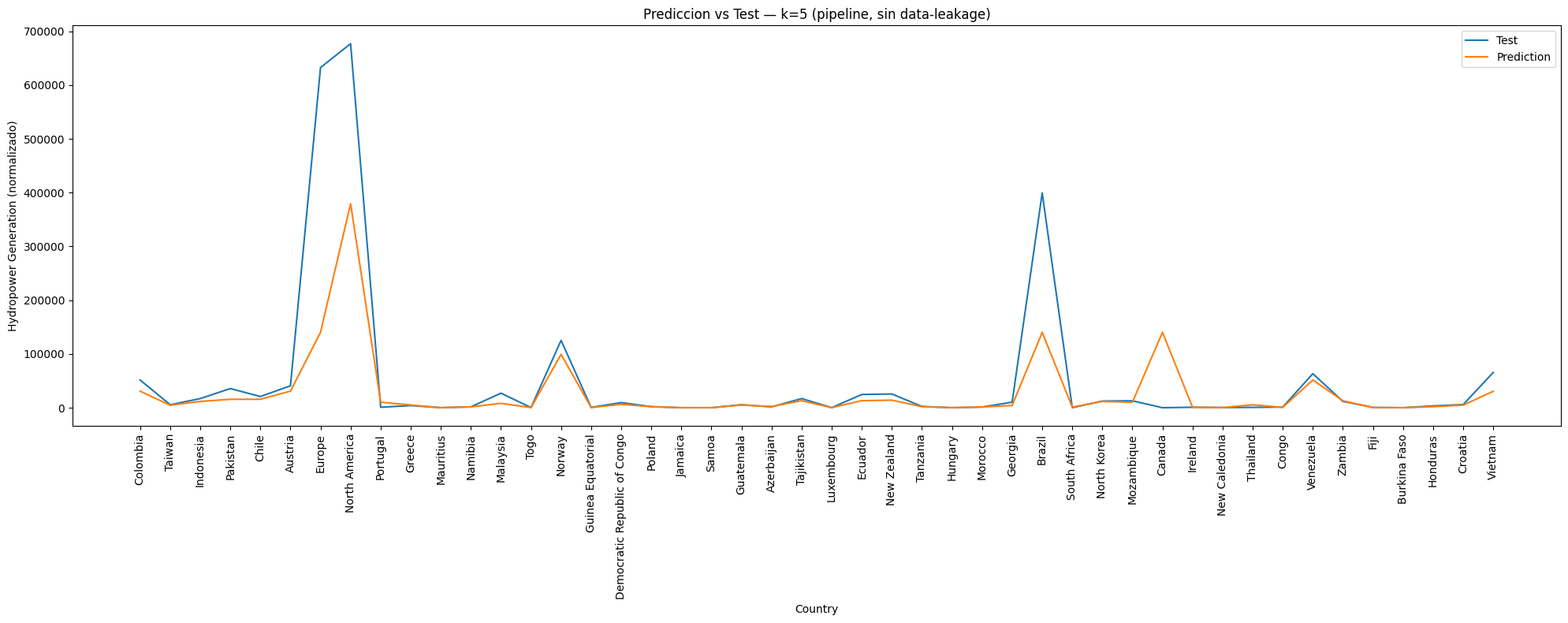
Puntos fuertes, puntos débiles y parámetros
En principio, hay dos parámetros importantes en el clasificador
KNeighbors: el número de vecinos y cómo se mide la distancia entre los puntos de datos. En la práctica, utilizar un número pequeño de vecinos, como tres o cinco, suele funcionar bien, pero se debería ajustar este parámetro.La elección de la medida de distancia correcta es también crucial. Por defecto,
KNeighborsutiliza la distancia euclidiana, que funciona bien en muchos casos. Uno de los puntos fuertes de \(k\)-NN es que el modelo es muy fácil de entender, y a menudo da un rendimiento razonable sin necesidad de muchos ajustes. El uso de este algoritmo es un buen método de referencia para probar, antes de considerar técnicas más avanzadas.La construcción del modelo de vecinos más cercanos suele ser muy rápida, pero cuando el conjunto de entrenamiento es muy grande (ya sea en número de características o en número de muestras) la predicción puede ser lenta. Cuando se utiliza el algoritmo \(k\)-NN, es importante pre-procesar los datos, tema que revisaremos en secciones posteriores. Este enfoque no suele funcionar bien en conjuntos de datos con muchas características (cientos o más), y lo hace especialmente mal con conjuntos de datos en los que la mayoría de las características son 0 la mayor parte del tiempo (los llamados conjuntos de datos dispersos).
Por lo tanto, aunque el algoritmo de \(k\)-vecinos más cercanos es fácil de entender, no se utiliza a menudo en la práctica, debido a que la predicción es lenta y a su incapacidad para manejar muchas características.
2.10. Proyecto Integrador de Aprendizaje Automático#
2.10.1. Predicción del riesgo de abandono académico en estudiantes universitarios#
2.10.1.1. Objetivo general#
Desarrollar modelos de regresión y clasificación supervisada usando K-Nearest Neighbors (KNN) para:
Estimar la probabilidad de abandono de un estudiante (clasificación binaria).
Predecir su índice acumulado esperado al final del semestre (regresión continua).
2.10.1.2. Contexto realista#
Una universidad desea anticiparse al riesgo de desersión de estudiantes de primer año para implementar acciones preventivas. Cuenta con datos históricos de cohortes pasadas incluyendo rendimiento académico, características socioeconómicas y hábitos de estudio.
2.10.1.3. Variables disponibles#
Tipo |
Variables |
|---|---|
Socioeconómicas |
Edad, estrato, tipo de colegio, ciudad de origen |
Académicas |
Puntaje de admisión, promedio de colegio, materias reprobadas |
Hábitos |
Asistencia promedio (%), uso de biblioteca, horas de estudio semanales |
Resultado target |
|
2.10.1.4. Tareas#
Preprocesamiento
Normalización/estandarización de variables
Codificación de variables categóricas (si las hay)
Modelado KNN
Aplicar KNN para clasificación (
abandona)Aplicar KNN para regresión (
promedio_final)Probar manualmente con varios valores de
k(ej: 3, 5, 7, 9, 11)
Evaluación de clasificación
Matriz de confusión
Accuracy, precision, recall, F1-score
Curva ROC y AUC
Análisis de impacto de
ken el desempeño
Evaluación de regresión
MAE, RMSE, R²
Gráfico: predicción vs. valor real
Impacto de
ken el error de predicción
Informe final
Comparar ambos modelos
Determinar qué valor de
kofrece el mejor compromiso para cada casoReflexión sobre ventajas y limitaciones del método KNN en contextos reales
2.10.1.5. Restricciones didácticas#
No se permite uso de
GridSearchCVSe debe usar
train_test_splity validación manualSe deben incluir gráficos con
matplotliboseabornEl código debe ser modular y reproducible
2.10.1.6. Herramientas sugeridas#
pandas,numpy,scikit-learnmatplotlib,seabornDataset simulado o real proporcionado por el docente
2.10.1.7. Resultado esperado#
Un notebook bien documentado, con análisis completo, visualizaciones claras y justificación de cada decisión. Ideal para evaluación en proyectos de fin de módulo o trabajos individuales.
2.10.2. Dataset recomendado: “Predict Students’ Dropout and Academic Success” (UCI)#
Fuente: UCI Machine Learning Repository, con 4,424 instancias y 36 características
Enlace: https://archive.ics.uci.edu/dataset/697/predict+students+dropout+and+academic+success
2.10.2.1. Ventajas clave#
Datos reales, sin valores faltantes
Ideal para tareas de clasificación y regresión
Compatible con métricas y visualizaciones comunes
2.10.2.2. Instrucciones de descarga#
Visitar el repositorio: https://archive.ics.uci.edu/dataset/697
Descargar el archivo CSV original
Compartir con estudiantes junto con descripción de variables
2.10.2.3. Ejemplo de variables#
Demográficas: edad, nacionalidad, estado civil, tipo de colegio
Académicas: nivel educativo previo, promedio de ingreso, materias reprobadas
Resultados:
academic_status(dropout / enrolled / graduate) → clasificaciónfirst_semester_gradeo similar → regresión
2.10.2.4. Diseño sugerido del notebook#
Análisis Exploratorio de Datos
Preprocesamiento
División de datos (
train_test_split)KNN clasificación: matriz de confusión, métricas, curva
ROCKNN regresión: métricas, predicciones vs valores reales
Comparación de distintos valores de
kDocumentación y conclusiones
2.10.2.5. Métricas#
Clasificación
Métrica |
Qué mide |
Cuándo usarla |
|---|---|---|
Accuracy |
Proporción de predicciones correctas sobre el total |
Datos balanceados y cuando todos los errores tienen el mismo costo |
Precision |
De las predicciones positivas, cuántas fueron realmente positivas |
Importante si los falsos positivos son costosos (ej: spam, diagnósticos falsos) |
Recall |
De los positivos reales, cuántos fueron detectados correctamente |
Importante si los falsos negativos son costosos (ej: enfermedades graves) |
F1-score |
Media armónica entre precision y recall |
Clases desbalanceadas; necesitas balancear precisión y cobertura |
ROC AUC |
Capacidad del modelo para distinguir entre clases |
Comparar modelos, especialmente si los umbrales cambian |
Matriz de confusión |
Muestra aciertos y errores por clase |
Siempre útil para entender los tipos de error |
Balanced Accuracy |
Promedio del recall de cada clase |
Dataset desbalanceado |
Regresión
Métrica |
Qué mide |
Cuándo usarla |
|---|---|---|
MSE (Mean Squared Error) |
Promedio de los errores al cuadrado |
Penaliza más los errores grandes; útil para comparar modelos durante el entrenamiento |
RMSE (Root Mean Squared Error) |
Raíz cuadrada del MSE |
Interpretación más intuitiva (en las mismas unidades que la variable objetivo) |
MAE (Mean Absolute Error) |
Promedio del valor absoluto de los errores |
Menos sensible a outliers que MSE; más robusto en datos con valores atípicos |
R² (Coeficiente de determinación) |
Proporción de la varianza explicada por el modelo |
Muy común para comparar modelos; varía entre -∞ y 1 (1=ajuste perfecto; <0=peor que promedio) |
Adjusted R² |
R² penalizado por el número de predictores |
Mejor para modelos con diferente número de variables; evita sobreajuste por exceso de variables |
MAPE (Mean Absolute Percentage Error) |
Error absoluto medio expresado en porcentaje |
Útil si te interesa interpretar los errores como porcentaje; cuidado con valores cercanos a cero |
Mediana AE (Median Absolute Error) |
Mediana del valor absoluto de los errores |
Aún más robusto a outliers que MAE |
2.10.2.6. Resumen#
Dataset |
Tareas |
Tamaño |
Ventajas clave |
|---|---|---|---|
UCI Student Dropout & Academic Success (UCI ML) |
Clasificación y regresión |
4,424 |
Real, sin valores faltantes, variables múltiples |
